Abstract
Euptychiina is considered a taxonomically difficult group given a high diversity of species and morphological homogeneity among them, making their identification complex. In this sense, DNA sequences offer a useful tool for species differentiation, providing valuable and complementary information to traditional morphological characters. The molecular characterization of thirteen Euptychiina species common to the northern Central Cordillera of the Colombian Andes was carried out using mitochondrial DNA sequences of the 3’ Cyt b gene, the tRNASer and the terminal portion of 3’ ND1. Sequences of the DNA fragments exhibited a degree of variation adequate for differentiating all species. Nucleotide variation was less than 2% at the intraspecific level and greater than 4% at the interspecific level. Additionally, an intergenic spacer was found in the Cyt b and the tRNASer that has not previously been reported for the Nymphalidae. Nucleotide variation in the spacer at the interspecific level was similar and complementary to that found in the coding region. The sequenced fragment is presented as a new tool to improve and complement taxonomic studies in groups like this, which include morphologically similar species. The proposed region combines various genes with different degrees of nucleotide variation, providing useful information for species identification.
Introducción
Euptychiina es uno de los grupos más diversos de Satyrinae con 42 géneros válidos y cerca de 400 especies descritas (Lamas 2004; Freitas y Peña 2006). Se le considera muy difícil taxonómicamente (Murray 2001; Peña y Lamas 2005) debido a la alta diversidad de especies, la existencia de muchos géneros mal definidos y la aparente homogeneidad morfológica entre especies relacionadas (Peña y Lamas 2005).
En géneros como Pareuptychia Foster (1964), la similitud morfológica entre sus especies y la gran variabilidad intraespecífica que se encuentra en estadios larvales y adultos hace aun más difícil su identificación (Murray 2001). En este sentido, la utilización de secuencias de ADN proporciona una herramienta útil para la diferenciación de sus especies (Murray 2001; Sperling 2003; Hebert
El ADN mitocondrial ha sido ampliamente usado en estudios evolutivos, poblacionales (Sperling 2003; Simon
Entre los genes mitocondriales, el que codifica para la subunidad b de la citocromo oxidasa (Cyt b), ha mostrado una apropiada resolución filogenética a nivel intragenérico e intergenérico (Simmons y Weller 2001). Específicamente en Satyrinae se ha empleado la región 5' de este gen para estudiar las relaciones evolutivas entre géneros y especies encontrándose una adecuada tasa de variación a este nivel taxonómico (Torres
En el presente estudio se realizó una caracterización molecular de trece de las especies de la subtribu Euptychiina más comunes en el norte de la cordillera central de los Andes colombianos, empleando secuencias de ADN mitocondrial de la región 3' del gen de la citocromo oxidasa subunidad b (Cyt b), incluyendo un gen de ARN de transferencia para Serina UCN (ARNtser) y el extremo 3' del NADH deshidrogenasa subunidad uno (ND1).
Materiales y Métodos
Obtención de secuencias de ADN.
Se obtuvieron muestras de trece especies pertenecientes a ocho géneros de Euptychiina y además se obtuvo un muestra de una especie de Haeterini (Cithaerias pireta Stoll, 1780) (Tabla 1) empleada como grupo externo. Todos los especímenes se recolectaron entre los años 1997 y 2001 en el extremo norte de la Cordillera Central y Valle del Magdalena Medio y depositados en el MEFLG. El ADN se extrajo de una de las patas media y posterior o en casos más difíciles de una porción del tórax removida cuidadosamente de las mariposas preservadas en seco a -20°C, las cuales se procesaron con buffer de lisis (Uribe 1999).
La amplificación de la porción de ADN seleccionada incluyendo el Cyt b, ARNtser y ND1 se realizó con oligonucleótidos cebadores diseñados por Beard
Análisis molecular
Las secuencias de nucleótidos se encuentran depositadas en la base de datos de Genbank (Tabla 1). Para su análisis, se realizó un alineamiento múltiple usando como referencia el genoma mitocondrial de
A partir del alineamiento se calculó el modelo de evolución de las secuencias en jModeltest 0.1.1. (Posada 2008; Guindon y Gascuel 2003), que fue empleado para la obtención del dendrograma de distancias génicas con el método de Neighbor-Joining (NJ) (Saitou y Nei, 1987) en el programa PAUP 4.0b10 (Swofford 2003). Usando el programa MEGA 4.0 (Kumar
Por último se realizó un análisis filogenético exploratorio de la región secuenciada. Para éste se tomó como grupo externo a
Resultados y Discusión
Caracterización de las secuencias.
En total se obtuvieron 42 secuencias de Euptychiina correspondientes a la región 3' del gen Cyt b, la secuencia completa del ARNtser (UCN) y un fragmento del extremo 3' de ND1. Se encontró variación en la longitud de las secuencias entre las especies. A nivel intraespecífico la variación fue mínima, solo se encontró en dos nucleótidos (nt) al interior de
Información de los especímenes usados para el análisis molecular.
Metros sobre el nivel del mar.
Cada una de las regiones amplificadas presentó distintos niveles de variación en su longitud (Tabla 2). La región 3' del gen Cyt b mostró un número de nucleótidos constante de 299 nt, el ARNtser (UCN) varió en su longitud desde 65 nt en el género
El número invariante de nucleótidos de Cyt b, posiblemente es ocasionado por la alternación en el producto codificado entre dominios intra y extramembrana, con distintas características funcionales o estructurales que varían entre dominios, causando que el tamaño de la proteína tenga una presión de selección sobre su longitud (Jermiin
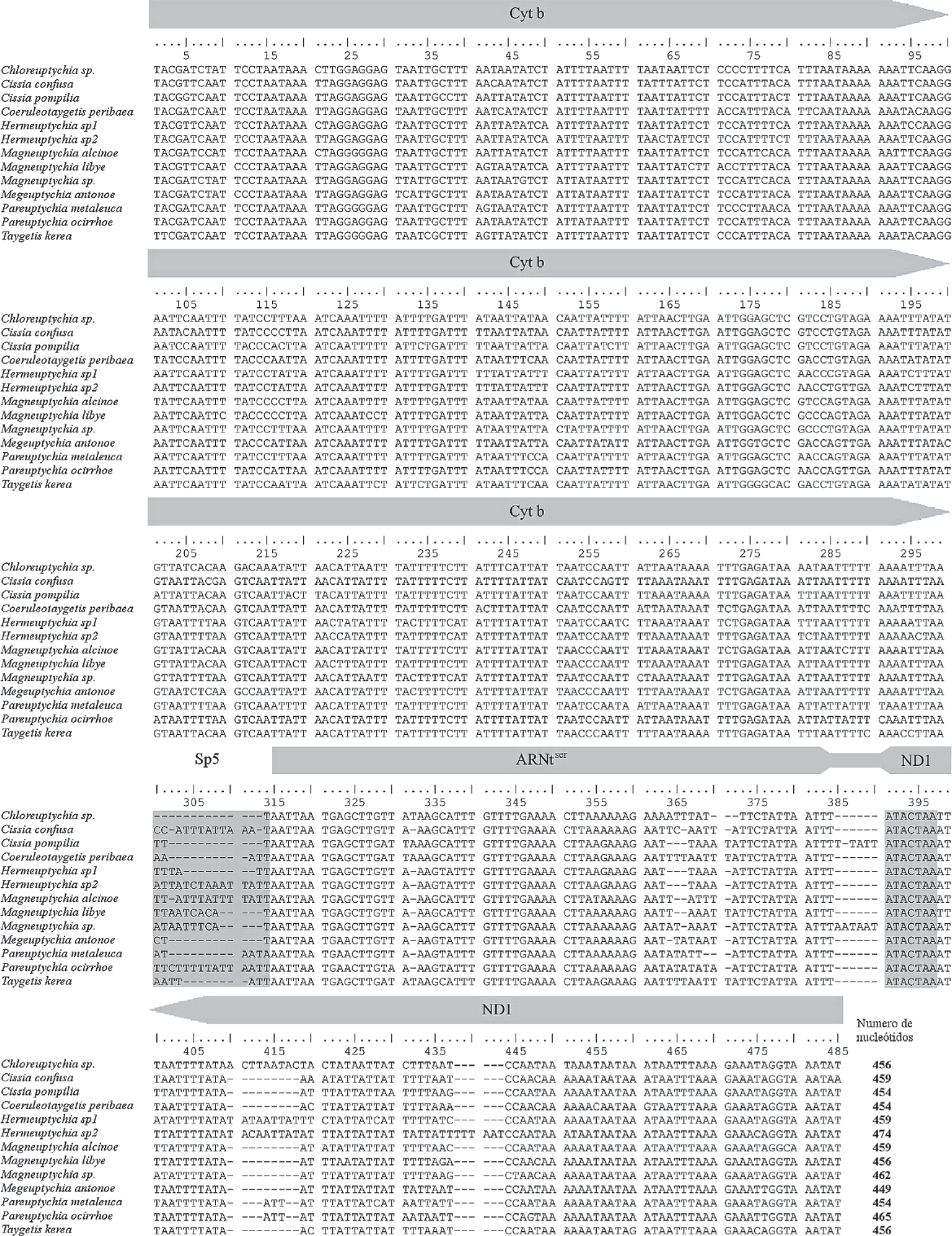
Secuencias de los genes Cyt b + ARNtser + ND1 en Euptychiina, resaltando con sombreado en gris a Sp5 y la región conservada de reconocimiento del gen ND1.
En promedio las secuencias presentaron un alto contenido de adenina y timina (A+T) que en Cyt b fue de 81,7%, para ARNtser de 83,3% y en ND1 de 90,7%, correspondiendo con lo encontrado previamente para los genes mitocondriales en Lepidoptera como
Número de nucleótidos de cada fragmento. Citocromo oxidasa subunidad b (Cyt b), espaciador intergénico 5 (Sp5), ARN de transferencia para serina UCN (ARNtser) y NADH deshidrogenasa subunidad uno (ND1).
El análisis de variabilidad nucleotídica reveló para el gen Cyt b 91 sitios polimórficos con 47 sustituciones no sinónimas y el test de Fisher mostró que este segmento del gen está sometido una selección de tipo neutral, con una variación homogénea en la mayor parte del fragmento (Fig. 2A), presentando un incremento de la entropía en las posiciones nucleotídicas 110-120 y 150-160, que corresponden a regiones de gran variabilidad al ser parte de la estructura de la proteína (Jermiin
A partir del espaciador Sp5 se observa un aumento en la variabilidad de las secuencias, en especial en las posiciones nucleotídicas 300 a 314 correspondientes a Sp5, de la 363 a la 370 del ARNtser y de la 410 a la 435 del ND1, debido principalmente a inserciones o deleciones. La región correspondiente a Sp5 presentó variación a nivel interespecífico, permitiendo diferenciar especies que son morfológicamente similares, como
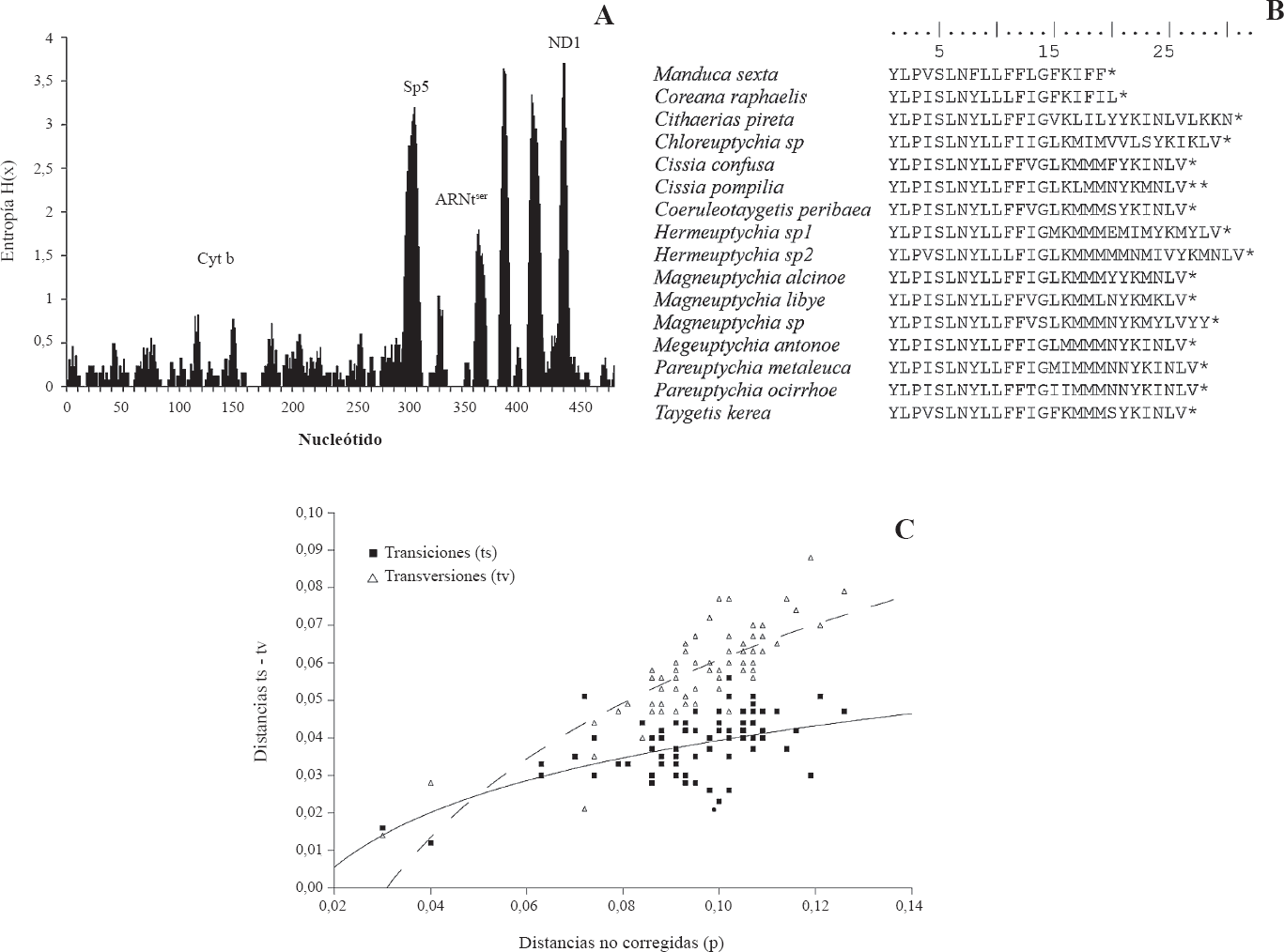
A. Entropía H(x) de la secuencia de nucleótidos de la región amplificada. B. Variación de la secuencias de aminoácidos del extremo carboxilo de ND1. C. Distancias no corregidas (p) para las secuencias en relación a las tasas de transiciones y transversiones.
Para el gen ND1, el test de Fisher indica que está sometido a una selección de tipo neutral. Para esta región se observaron 49 sitios polimórficos con 18 sustituciones no sinónimas, siendo la región que proporcionalmente presentó la mayor variabilidad por nucleótido. El análisis de entropía revela que la variabilidad está concentrada en las posiciones 385-390 y 410-445. Comportamiento en el extremo 3' del ND1, ocasionado por la carencia del espaciador 6 (Sp6) entre los genes ND1 y ARNtser, reportado comúnmente en Lepidoptera (Cameron y Whiting 2008). La ausencia de este espaciador es debida a un cambio del codón de terminación del gen ND1, el cual se encuentra en límites del gen ARNtser con una sobreposición de dos nucleótidos entre ambos genes.
El cambio en el codón de parada de ND1 causa la traducción de Sp6, que es verificada por la traducción de la región conservada ATACTAA (Fig. 1) en las posiciones 392 a 398, que normalmente se presenta en Sp6 de Lepidoptera (Cameron y Whiting 2008). Esta región cumple una función esencial para el reconocimiento del gen por la ARN polimerasa (Taanman 1999). Este cambio resultaría en una proteína de mayor longitud en el extremo carboxilo (Fig. 2B) pero que no debe causar alteraciones en la actividad catalítica de la proteína debido a que el extremo carboxilo cumple una función estructural y normalmente se reporta como la región más variable del gen (Videira y Duarte 2001; Dupuis
Distancias génicas y análisis filogenético.
La relación entre transiciones/transversiones (Fig. 2C), mostró un aumento gradual de las tasas de sustitución nucleotídica con respecto a las distancias génicas entre las especies, especialmente de las transversiones, aunque sin presentar saturación de sustituciones. Todo esto sugiere que el fragmento secuenciado es apropiado para el nivel taxonómico al cual se realiza el estudio.
La diferencias nucleotídicas entre géneros variaron de 6,5 a 13,7%, entre especies de 4,5 a 10,6% (Tabla 3) y dentro de las especies de 0 a 1,8%. Resultados similares han sido obtenidos por Torres
Valores de distancias no corregidas (p).
Los porcentajes de divergencia nucleotídica a nivel intra e interespecífico presentaron una marcada distancia, pero a nivel intergenérico no existe una clara diferenciación, fenómeno particularmente visible entre los géneros y especies de
El modelo de evolución molecular calculado con jModeltest 0.1.1 (Guindon y Gascuel 2003; Posada 2008) correspondió al GTR (General Time Reversible) (Rodríguez
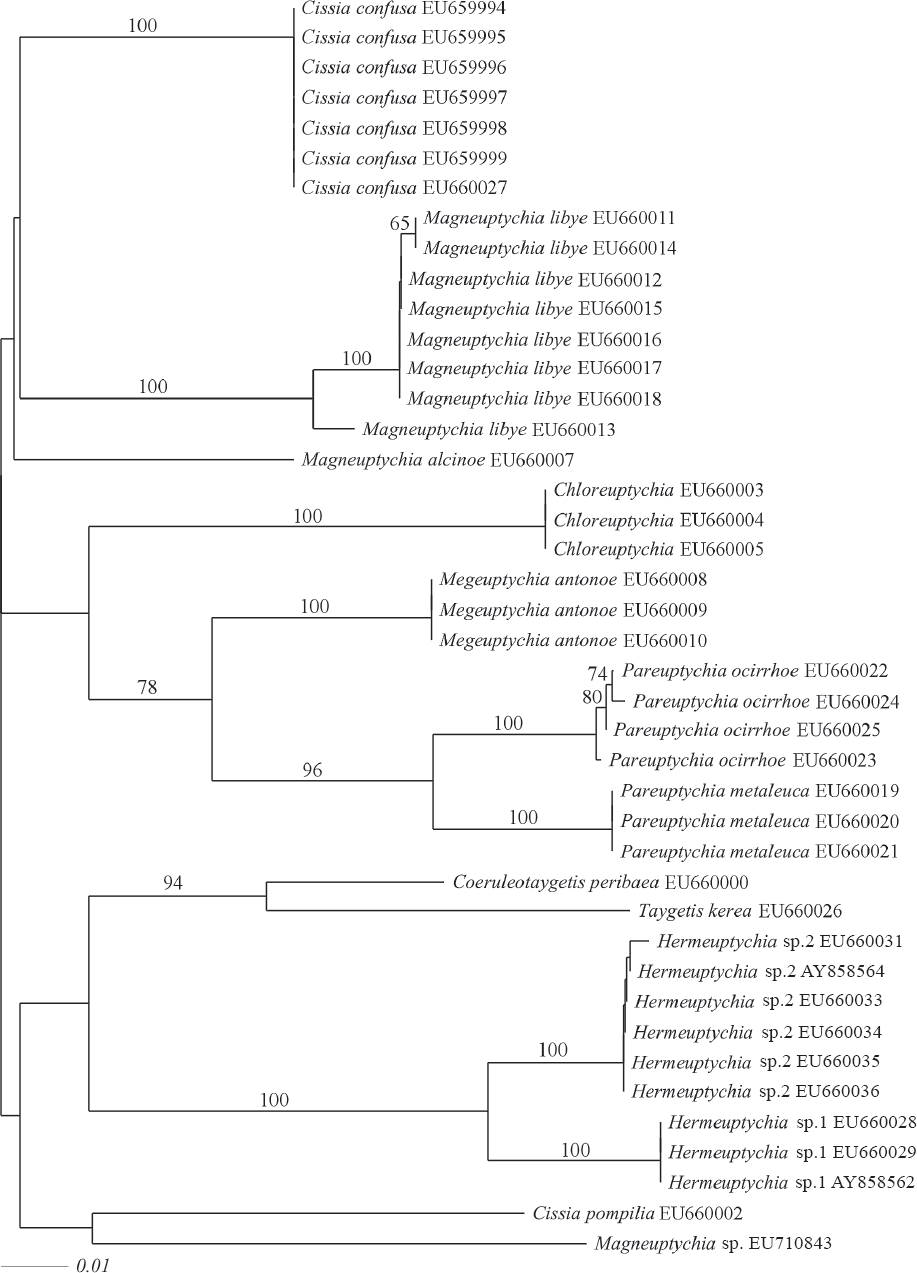
Dendrograma de NJ con el modelo GTR+G y bootstrap de 1000 réplicas, mostrando solo los valores superiores al 50% de las secuencias de Cyt b + ARNtser+ ND1 las 13 especies de Euptychiina.
Los los árboles filogenéticos (Fig. 4), recobran los clados
Las relaciones filogenéticas entre géneros no se encuentran resueltas, en gran parte debido al reducido muestreo taxonómico y a la falta de un mayor número de caracteres, El análisis de máxima parsimonia (Fig. 4A) presenta una politomía entre géneros, y el análisis bayesiano (Fig. 4B) obtiene a
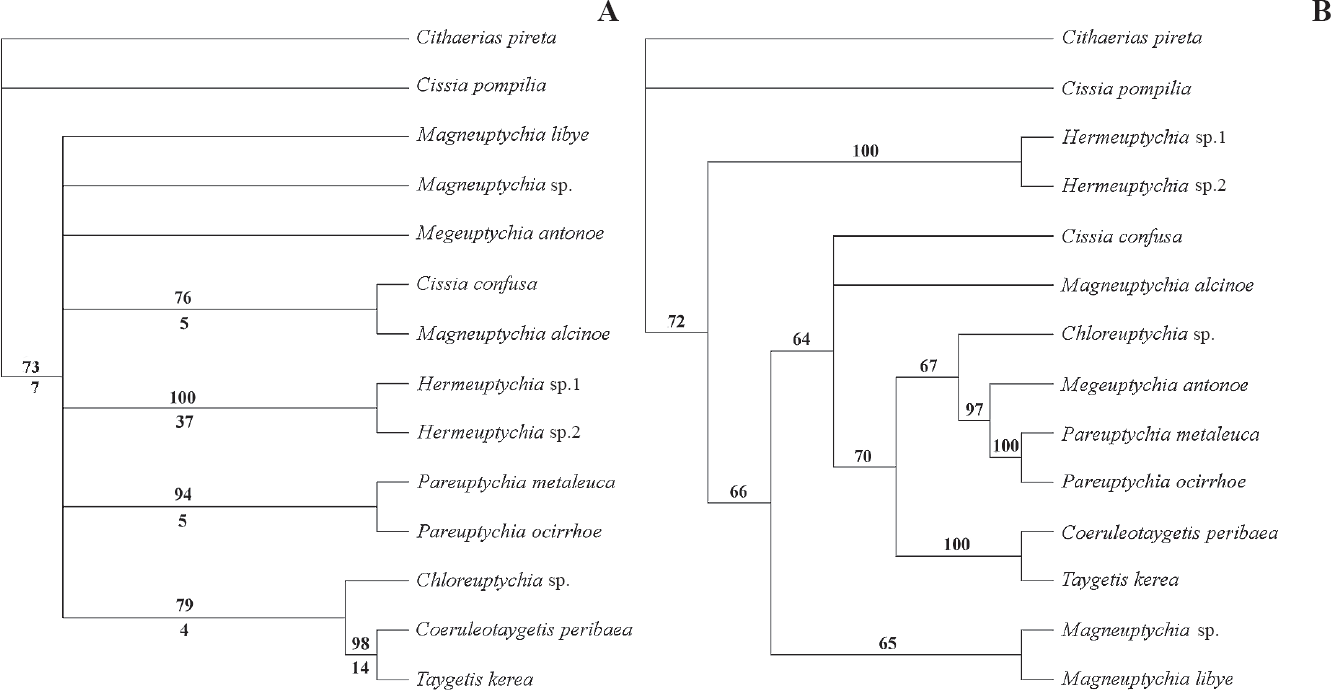
Análisis filogenético con las secuencias de Cyt b + ARNtser + ND1 de Euptychiina. A. Consenso de los dos árboles más parsimoniosos (longitud de 432, CI: 0.6042, RI: 0.4083), soporte de nodos con bootstrap indicado en la parte superior y soporte de Bremer en la parte inferior. B. Inferencia Bayesiana con 10.000.000 de cadenas Markovianas y el modelo GTR+G (forma gamma = 0.2030). Se muestran los valores de bootstrap y probabilidad posterior superiores al 50%.
Conclusiones
El fragmento de ADN mitocondrial correspondiente a la región 3' de Cyt b, el gen completo de ARNtser y el extremo 3' de ND1, muestra ser eficaz para la diferenciación de las especies de Euptychiina. Siendo de utilidad para la diferenciación de especies debido principalmente a que presenta gran variabilidad con un modo de selección de tipo neutral y combina genes con distintas funciones en la mitocondria, brindando independencia a las mutaciones presentes entre las regiones amplificadas. Características que posibilitan su empleo en estudios de diversidad de mariposas y que mediante la combinación con otros genes comúnmente usados en estudios taxonómicos como el gen COI, permitirían una mayor resolución y confianza a estos análisis.
El presente estudio sugiere la presencia de especies muy similares morfológicamente (crípticas), en algunos géneros de Euptychiina, que pueden ser diferenciadas con la ayuda de datos moleculares. Como es el caso del género
Footnotes
Agradecimientos
Agradecemos a Luz Miryam Gómez por su asistencia en el trabajo de laboratorio, Carlos Federico Álvarez por su colaboración para la obtención de los ejemplares, a Carlos Peña, Blanca Huertas, Ana María Vélez y Alejandro Ramírez por los comentarios realizados y a dos evaluadores anónimos por sus críticas constructivas que enriquecieron el análisis del manuscrito. Este trabajo se realizó con el apoyo de la Dirección de investigaciones DIME, Universidad Nacional de Colombia, sede Medellín y André V. L. Freitas agradece a la Fapesp (04/05269-9), al CNPq (300282/2008-7) y a la National Science Foundation (DEB-0527441) por los auxilios financieros.
