Abstract
Twenty-three silkworm
Introducción
Dentro de las diversas variedades de polillas que secretan fibras de seda, se incluyen
El “stock” genético del gusano de seda domesticado lo componen un gran número de ecotipos y líneas autocruzadas artificialmente que se distribuyen en regiones templadas (líneas que presentan diapausa) y tropicales (líneas sin diapausa). Estas variedades difieren, entre otros, en los caracteres cualitativos y cuantitativos que afectan la calidad de la seda. Las líneas sin diapausa son pobres productoras de seda, presentan crecimiento rápido, peso corporal bajo y fibras de seda gruesas y cortas, son resistentes y se sabe que se pueden desarrollar aún en condiciones desfavorables como las encontradas en regiones tropicales con temperaturas altas y humedad alta propicias para condiciones de sanidad baja y el desarrollo de pestes y enfermedades. Las líneas tropicales de gusano de seda, sin embargo, presentan un gran número de crías al año; es decir, son polivoltinas, lo que de alguna manera compensa su productividad baja. Las líneas con diapausa, producen mayor cantidad de seda y de mejor calidad, presentan una vida larval larga, peso corporal alto y fibras de seda largas y delgadas aunque sólo se pueden obtener una o máximo dos crías al año (uni o bivoltinas). En estas últimas, a pesar de ser mejores productoras de seda, su cría en regiones tropicales no es viable dada su alta susceptibilidad a pestes y malas condiciones de cría (Sharma
Dado el trabajo que con el gusano de seda se ha llevado a cabo desde hace muchos años, en este momento se cuenta con una gran cantidad de ecotipos y más de 3.000 líneas mejoradas, y aproximadamente 400 mutantes hereditarios muchos de los cuales ya han sido mapeados (Doira 1992). La identificación y explotación de los polimorfismos al nivel de secuencias de ADN es uno de los desarrollos más significativos de la biología molecular; este tipo de polimorfismos ha sido usado con éxito en diversas especies de plantas y animales, tanto en programas de mejoramiento como de identificación varietal, QTLs y mapeo genético. El uso de marcadores moleculares posee varias ventajas sobre la identificación por caracteres morfológicos, ya que no se afectan por el ambiente, y pueden ser identificados en cualquier estadio de desarrollo (Nagaraju 2000).
En el gusano de seda, se han empleado muchas técnicas para identificar el polimorfismo a nivel molecular, como el uso de marcadores enzimáticos, estudiando amilasas de hemolinfa en líneas de gusanos tropicales y de regiones templadas (Nagaraju 2000). Los análisis permitieron identificar polimorfismo electroforético de las amilasas anódicas como cuatro bandas en las líneas sin diapausa y cinco bandas en las líneas con diapausa; la banda extra en las líneas de regiones templadas corresponde a una banda de migración lenta. Cuando la separación es catódica, se identificó una sola banda en las líneas sin diapausa y ninguna en las líneas con diapausa. En este estudio también se pudo determinar que las líneas de diapausa excretan cinco veces más almidón que las líneas sin diapausa (Nagaraju 2000). Los estudios moleculares de ADN basados tanto en marcadores que usan PCR como en aquellos que no, analizando trece líneas de gusano de seda seis con diapausa y siete sin diapausa, permitieron la separación de los individuos claramente en dos ramas de un dendrograma, aquella de los individuos con diapausa y aquellos que no presentaban diapausa, al igual que permitió la identificación de marcadores exclusivos para cada uno de los dos grupos (Nagaraju
Materiales y Métodos
El estudio se desarrolló sobre 12 líneas de origen Japonés (KOI, K02, KO5, K10, K20, K30, K40, K522, SG3, SG2, NG, KNA) y 11 líneas de origen Chino (CA, CBS, CC, CJ, CGS, CHS, CLS, CTS, SC1, SC2, SC3), todas ellas pertenecientes al Centro de Desarrollo Tecnológico de la Sericultura (CDTS) mantenidas en la finca “El Pilamo”, Risaralda.
Extracción de ADN
El ADN genómico fue extraído de la porción posterior de la glándula serígena (Suzuki
AFLP y selección de iniciadores
Las reacciones de AFLP (Vos
Análisis estadístico
Las bandas de ADN se tomaron como un locus genético asumiendo además que los alelos marcadores de diferentes loci no comigran y que cada locus puede ser tratado como un sistema de dos alelos (Lynch y Milligan 1994). De esta manera, se construyeron matrices de datos con 1 para la presencia y 0 para la ausencia de cada uno de los loci. Los datos se organizaron y analizaron por separado en razón de su origen geográfico y dentro de cada una de estas poblaciones se definieron subpoblaciones basándose en su relación de agrupamiento en el dendrograma.
Similaridad y análisis de agrupamiento
La identificación de las relaciones para las 23 líneas de gusano analizadas se basó en las matrices construidas con los índices de similaridad (Nei y Li 1979). Los valores de disimilaridad se analizaron con el método de los pares de grupos no ponderados con media aritmética (UPGMA), y se construyó un dendrograma. Un análisis de componentes principales (Gower 1966) se llevó a cabo para mostrar la distribución de las relaciones en tres dimensiones. Todos estos análisis se hicieron usando NTSYS-pc ver. 2.01 (Rohlf 1998).
Estadística descriptiva y diversidad
Antes de correr cada uno de los análisis el supuesto de homoscedasticidad (homogeneidad de varianzas) fue revisado mediante una prueba de Bartlett (Sokal y Rohlf 1981). Los programas POPGENE, ver. 1.32 (Yeh
Estructura poblacional
El programa AMOVA-PREP (Miller 1998) se usó para transformar el conjunto de datos dominantes para el programa de Análisis Molecular de Varianza (AMOVA, ver. 1.55; Excofier
Distancia genética
La distancia genética se evaluó sobre las poblaciones y subpoblaciones con el programa TFPGA (Tools for Population Genetic Analysis), ver. 1.3 (Miller 1999), empleando el cálculo descrito por Nei (1978).
Resultados
Similaridad y análisis de agrupamiento
La organización de los datos se llevó a cabo definiendo subpoblaciones dentro de cada una de las razas determinadas a través de la relación en el dendrograma y analizando además solamente dos poblaciones correspondientes a cada una de las razas geográficas. La significancia en la escogencia de estos grupos se comprobó estadísticamente con la prueba exacta de diferenciación de poblaciones (Raymond y Rousset 1995), encontrándose que el nivel de estructuración correspondiente a subpoblaciones no era significativo, pero sí el nivel de población. Los análisis individuales de cada una de las combinaciones usadas arrojaron resultados similares y presentaron índices de correlación entre los datos de las diferentes matrices superiores al 90%, lo que significa que el número de combinaciones empleadas es suficiente para explorar la diversidad presente en estas líneas de gusano de seda. El nivel de polimorfismo para las combinaciones estuvo en el rango 65,6-75,8%, aunque se generó un gran número de fragmentos de restricción (247 bandas), a partir de las muestras individuales con la técnica de AFLP (Tabla 1). Solamente se usaron para el análisis, aquellos fragmentos que fueron polimórficos y se registraron sin ambigüedad; esta corrección se hizo según el criterio establecido por Lynch y Milligan en 1994 analizándose finalmente 168 bandas de los datos totales con un promedio de polimorfismo de 90,4% (Tabla 2). El resto de los análisis se llevaron a cabo solamente para los datos corregidos.
Análisis de las combinaciones de AFLP usadas.
Análisis de estadística descriptiva para cada una de las combinaciones y para la sumatoria de estas combinaciones.
El dendrograma generado por el análisis de UPGMA de las 168 bandas para las cuatro combinaciones de iniciadores resolvió las 23 líneas de gusano de seda en dos grupos perfectamente definidos como raza japonesa y raza china (Fig. 1), a una distancia de 0,22 para las muestras de la raza japonesa y 0,18 para las muestras de la raza china. El análisis permitió identificar perfectamente cada uno de los individuos; sin embargo, en la rama correspondiente a la raza japonesa se obtuvieron dos líneas (K02, SG2) que presentaron patrones de AFLP casi idénticos, distancia igual a 0,08 (Figs. 1 y 2).
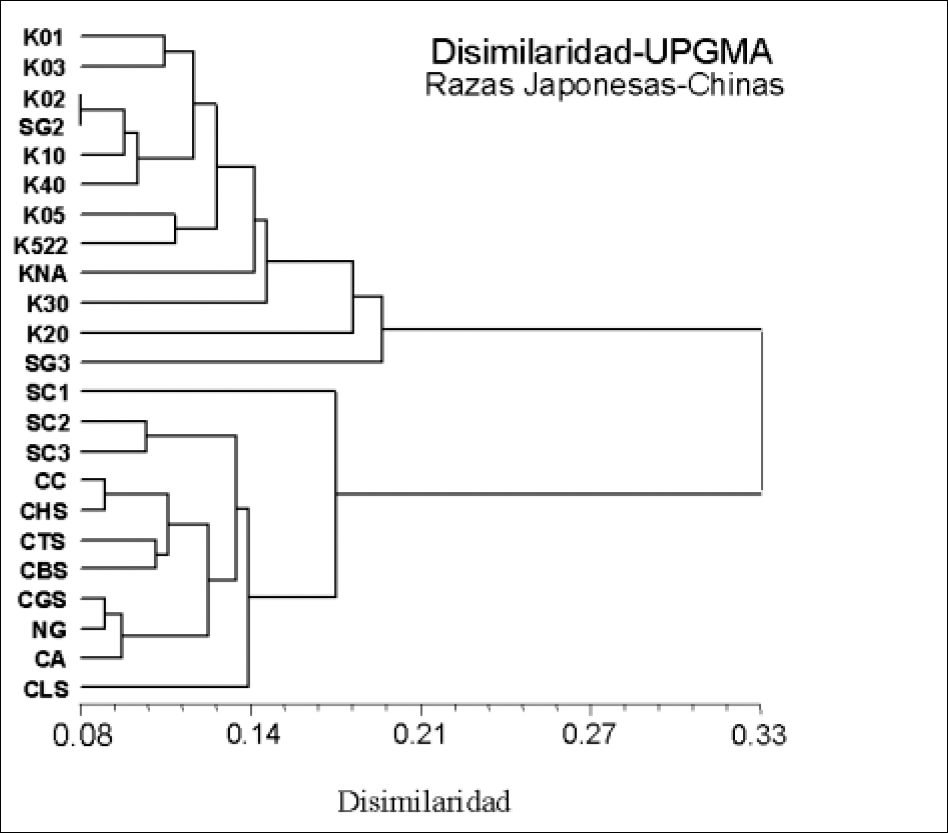
Dendrograma derivado de UPGMA que ilustra las relaciones entre las 23 líneas de las dos razas de gusano de seda
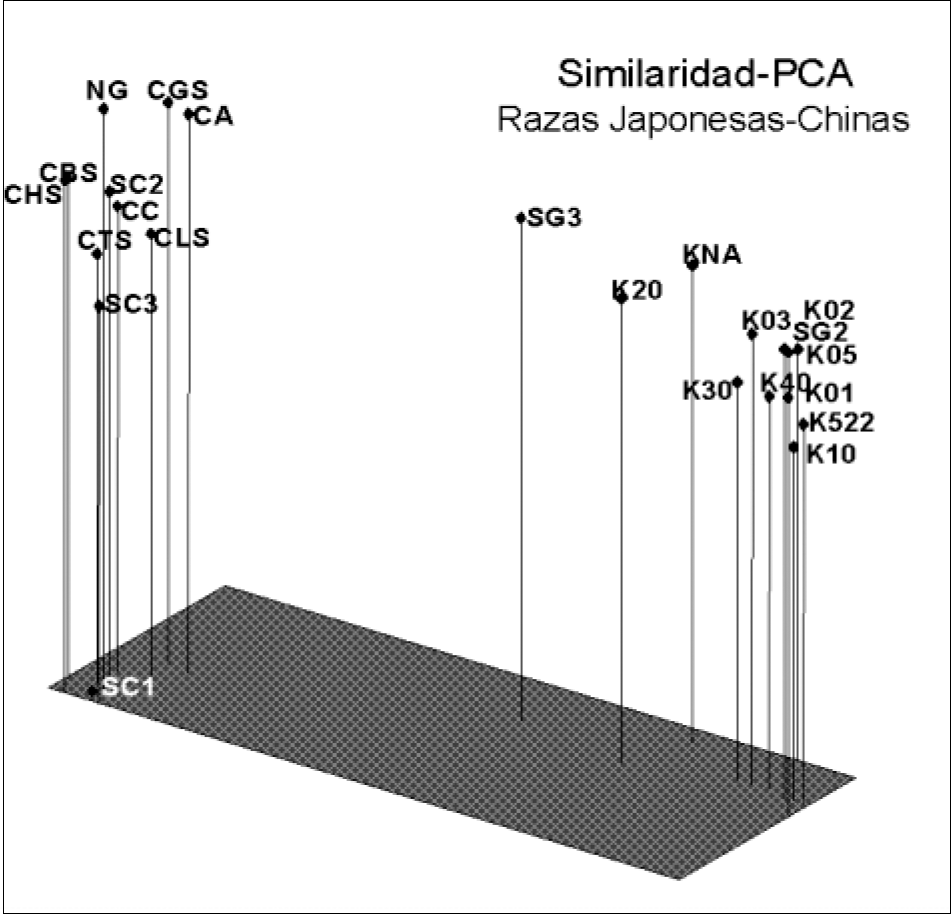
Análisis de componentes principales, una matriz de apareamiento simple, para los datos de similaridad obtenidos a partir de los análisis de 168 bandas de AFLPs.
Estadística descriptiva y diversidad
El conjunto de datos obtenido con las cuatro combinaciones de iniciadores muestra en el dendrograma y en el análisis de componentes principales, que la rama correspondiente a la raza japonesa es más heterogénea que la de la rama de la raza china. Esta observación es confirmada con los datos de heterocigocidad, los cuales siempre son mayores para las líneas de raza japonesa que para las líneas de raza china. El estimado del grado de diferenciación poblacional establecido por el valor Gst para cada uno de los loci indica un grado alto de diferenciación (Tabla 3).
Estructura poblacional
Los componentes de varianza se obtuvieron a partir de las muestras corregidas, con el programa AMOVA, ver. 1.55. (Excofier
Discusión y Conclusiones
En el presente estudio se demuestra que la técnica de AFLPs puede ser usada exitosamente en gusano de seda para revelar polimorfismos a nivel del ADN útiles y que en algún momento pueden ser considerados como marcadores genéticos. Los resultados demuestran que esta técnica es valiosa en la identificción de la variabilidad genética en el gusano de seda. En general, la información arrojada por cada una de las combinaciones parece ser la misma, por lo cual se puede decir que el análisis parece estar abarcando la totalidad del genoma del gusano de seda. El análisis ha permitido la identificación de bandas específicas para cada una de las razas estudiadas, las cuales pueden tener gran utilidad en establecimiento de derechos de propiedad intelectual y la determinación de pureza del germoplasma tanto en las líneas puras como en los híbridos obtenidos para uso comercial.
Los conglomerados formados identificaron perfectamente las líneas sobre la base de su origen geográfico, indicando claramente los componentes japonés y chino de cada una de las líneas, los cuales, parecen estar acentuados debido a la estrategia de cómo son mantenidas las líneas, a través de procesos de endogamia. A pesar de que la diversidad observada fue baja, menor al 10%, los resultados permiten sugerir que las líneas a partir de las cuales se está manteniendo la raza japonesa fueron originalmente menos homogéneas que aquellas con las cuales se mantiene la raza china. Sin embargo, en el grupo de origen japonés se identificaron dos líneas casi idénticas y aunque en las líneas chinas se presentan más líneas similares entre si, no se encontró ninguna con este grado bajo de diversidad. Las variedades geográficas de gusano de seda
Los resultados de los componentes de varianza sugieren que sí se quieren implementar programas de mejoramiento y de obtención de híbridos de mayor productividad, es necesario aumentar la base genética introduciendo nueva líneas ya sea del mismo o de diferente origen geográfico, que permitan un grado mayor de diversidad poblacional.
El gusano de seda, B. mori, comprende un gran número de ecotipos y líneas sintéticas endogámicas que muestran un alto grado de divergencia con respecto al origen geográfico, caracteres morfológicos, cuantitativos y cualitativos. Entonces, es importante el estudio de la diversidad genética de varios genotipos de gusano de seda con el propósito de adelantar un programa de mejoramiento de líneas.
AMOVA-CORREGIDA. Análisis de los componentes de varianza dentro y entre poblaciones de las muestras de gusano de seda
AMOVA-CORREGIDA. Análisis de los componentes de varianza dentro y entre poblaciones y subpoblaciones de las muestras de gusano de seda
Footnotes
Agradecimientos
Los autores agradecen el apoyo financiero por parte de COLCIENCIAS del proyecto con código 1110-12-11603 y de la Universidad Tecnológica de Pereira en el marco de la convocatoria en biotecnología.
