Abstract
Triatoma venosa is one of the main secondary vectors of Chagas Disease in Colombia. To study its genetic structure, 30 adult individuals of T. venosa were collected in the municipalities of Somondoco (villages of Cabrera and Barreras), Guateque (villages of Llano Grande, Tincachoque, and Cantoras) and Sutatenza (villages of Sisquique, Ovejeras, el Gaque and Piedra Larga) department of Boyaca, from two different habitats (peridomestic and domestic). Genomic DNA of each individual was amplified by RAPD using 4 primers; the products were visualized after polyacrilamide gel electrophoresis followed by 6% silver staining. The dendrogram obtained after analysis with SYNTAX 2000 and RAPDPLOT software did not define a cluster for each insect population evaluated. When the binary matrix was analyzed with RAPDFST software, the Wright's Fst was 0,047 and Weir & Cockerham's Fst was 0,056. The effective migration rate in this analysis was 5,0 under Wright's methodology and 4,2 under Weir & Cockerham's methodology. These preliminary results indicate a high mobility of the insects between the two habitats and a high genetic flow, which do not allow the establishment of genetic differentiation between the domestic and peridomestic populations analyzed.
Introducción
La enfermedad de Chagas fue descrita por primera vez por Carlos Chagas en 1909, es exclusiva del continente americano y es causada por Trypanosoma cruzi, un protozoo parásito flagelado trasmitido a humanos por insectos triatominos. La distribución geográfica de infecciones humanas por T. cruzi se extiende desde México hasta el sur de Argentina, afectando entre 16 a 18 millones de personas, adicionalmente cerca del 25% de la población latinoamericana se encuentra en riesgo de adquirir la enfermedad (WHO 2000). En Colombia se estima que alrededor del 5% de la población está infectada y cerca del 20% se encuentra bajo riesgo de adquirir la infección (Guhl 2000).
La transmisión de T. cruzi se lleva a cabo principalmente por medio de insectos vectores que han mostrado una fuerte estructuración geográfica, la cual puede ser detectada por marcadores morfométricos, citogenéticos e isoenzimáticos (Guhl y Schofield 1996). Adicionalmente, se han empleado marcadores moleculares generados por amplificación azarosa de polimorfismos de ADN que permiten detectar variabilidad genética entre diferentes poblaciones de vectores (Welsh y McCleland 1990; Williams et al. 1990).
Harry et al. (1998) realizaron una revisión sobre la utilización de RAPD (Random Amplified Polymorphic DNA) en entomología y sugirieron que estos marcadores son útiles en estudios de genética poblacional y pueden ser de gran utilidad en programas de control a través de la localización de genes o de regiones importantes en el genoma.
En triatominos, se han realizado algunos estudios utilizando esta técnica, Carlier et al. (1996) presentaron unos resultados preliminares sobre el uso de RAPD en la comparación de vectores triatominos intra e interespecíficos, los cuales permitieron una separación fácil entre Triatoma sordida y T. infestans, al igual que poblaciones silvestres y domésticas de T. infestans. De la misma manera, Jaramillo et al. (2001), usando esta misma técnica molecular, establecieron que no se presentaba flujo genético entre Rhodnius prolixus y R. colombiensis (domiciliados y silvestres, respectivamente), corroborando de esta manera las diferencias encontradas mediante métodos morfométricos y bioquímicos por Moreno et al. (1999). Otras especies de triatominos evaluadas de manera preliminar por esta técnica han sido T. brasiliensis (Borges et al. 2000) donde se sugiere una heterogeneidad poblacional y Triatoma dimidiata (Jaramillo et al. 2003) donde se sugiere homogeneidad genética entre las poblaciones domésticas, peridomésticas y silvestres de esta especie.
Estudios como los realizados para Rhodnius spp. y T. dimidiata evidencian la necesidad de evaluar la estructura genética de otras especies vectores en Colombia, permitiendo entender el comportamiento de sus poblaciones y de esta manera, poder establecer estrategias de control vectorial más eficaces.
En esta investigación se muestran resultados preliminares de la estructura genética de Triatoma venosa (Stål), un vector secundario de importancia epidemiológica por su amplia distribución geográfica (Guhl et al. 2002) y cuyos hábitos y hospederos son desconocidos. Hasta el momento, T. venosa ha sido registrado en forma silvestre en Ecuador (Azuay, Sucumbios, Napo) y en colonias domésticas en Colombia (Boyacá, Santander) (Abad-Franch y Aguilar 2003). Se empleó la técnica RAPD (Williams et al. 1990), con el fin de analizar la estructura genética y detectar variabilidad genética de poblaciones domésticas y peridomésticas de esta especie capturadas en el departamento de Boyacá, Colombia, para poder estimar el riesgo epidemiológico que representa la población peridoméstica en la transmisión de la enfermedad de Chagas en Colombia. Este estudio se llevó a cabo en el Centro de Investigaciones en Microbiología y Parasitología Tropical CIMPAT. Universidad de los Andes, Bogotá - Colombia, en el año 2003.
Materiales y Métodos
Los insectos evaluados se capturaron en dos hábitat diferentes: en gallineros localizados fuera de las viviendas habitadas o hábitat peridoméstico (15 individuos) y dentro de las viviendas o domicilio (15 individuos), para un total de 30 individuos adultos provenientes del departamento de Boyacá, en los municipios de Somondoco (veredas de Cabrera y Barreras), Guateque (veredas de llano grande, Tincachoque, y Cantoras) y Sutatenza (veredas de Sisquique, Ovejeras, el Gaque y Piedra Larga), localizados alrededor de los 1.700 msnm.
El procedimiento de extracción de ADN genómico total se realizó mediante la maceración de las seis patas de cada individuo, previamente lavadas con hipoclorito para evitar contaminación con ADN foráneo, seguida de una purificación mediante el kit Aqua Pure para el aislamiento de ADN a partir de tejidos de BIO-RAD®. EI ADN se almacenó a -20°C hasta el momento de su análisis. Se empleó el kit Ready To Go RAPD de Amersham Pharmacia®, rehidratando cada perla con 19 µl de agua destilada y agregando 25 pmol de iniciador (5 µl). Posteriormente, se dividió el contenido en cuatro tubos, a cada uno de los cuales se le agregaron 2 µl de ADN templado, para un volumen final de reacción de 8 ul. El perfil térmico utilizado consistió en: un paso inicial de denaturación a 95°C por 5 minutos, seguido de 44 ciclos de 95°C por 1 min, 36°C por 1 min, 72°C por 2 min y un paso final de elongación a 72°C por 7 min.
Se analizaron 15 individuos peridomésticos y 15 individuos domésticos con los iniciadores RTG 2, 3, 4 y 5 de Pharmacia® (Tabla 1), que permitieron obtener un total de 70 marcadores.
La visualización de los productos de RAPD se realizó en geles de poliacrilamida al 6% con un tiempo de corrido electroforético de 3 h a 80 V, los cuales fueron posteriormente teñidos con el kit Silver Stain Plus de Pharmacia® siguiendo el protocolo recomendado por el fabricante.
Se construyeron matrices binarias de datos de acuerdo con Welsh et al. (1992) en donde se representa la información genética colectada para cada individuo. La matriz de datos se analizó con los programas RAPDPLOT (Kambhampati et al. 1992) y SYNTAX2000 (Podani 1993), los cuales permiten crear una matriz de distancia empleando el índice de Disimilaridad de Jaccard. Posteriormente, esta matriz fue utilizada para construir un dendrograma mediante el algoritmo UPGMA (Unweighted Pair Group with Averaging).
Se empleó el programa de RAPDDIST para establecer las distancias genéticas de Nei (1973) entre poblaciones a partir de una matriz de datos y, posteriormente con la matriz de distancia, se generó el dendrograma con 1.000 repeticiones.
Secuencia de los iniciadores RTG de Pharmacia® utilizados en las reacciones de amplificación RAPD
Resultados
Con los 4 iniciadores empleados, no se observa un patrón de bandeo definido para ninguna de las dos poblaciones estudiadas (Fig. 1), similar a lo señalado en Triatoma dimidiata (Jaramillo et al. 2003), como sí se pudo establecer previamente para Rhodnius prolixus y R. colombiensis (Jaramillo et al. 2001), donde claramente se definían patrones particulares de polimorfismos mediante la técnica de RAPD para cada especie estudiada.
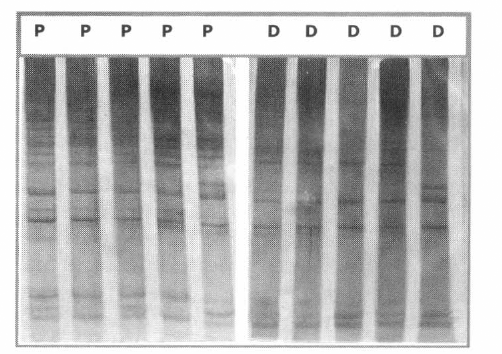
Geles de poliacrilamida al 6% teñidos con el kit Silver Stain Plus de Pharmacia®, donde se visualizan los productos de amplificación por RAPD con el iniciador RTG 5 de Pharmacia®, para cinco individuos peridomésticos (P) y cinco domésticos (D) de Triatoma venosa.
Para T. venosa se observa una homogeneidad en los patrones de bandeo entre las dos poblaciones evaluadas (Fig. 1), lo que sugiere una poca diferenciación genética entre las dos poblaciones estudiadas de este insecto.
El análisis mediante los programas SYNTAX 2000 y RAPDPLOT generó un dendrograma donde no se define un cluster para cada población de insectos, sino que se ve una distribución mezclada de los individuos de las diferentes poblaciones (Figs. 2-3).
Al realizar el análisis con el programa RAPDFST se calculó el Fst de Wright (1951) y de Weir & Cockerham (1984) (Tabla 2), para las dos poblaciones en conjunto. Con la metodología de Wright y de Weir & Cockherman, el Nm fue suficiente para mantener homogeneidad genética, debido a que al menos un individuo debe migrar por generación. Estos resultados indican una gran movilidad de los insectos entre los dos ambientes y un elevado flujo genético que no permite el establecimiento de diferenciación genética entre las dos poblaciones evaluadas.
Valores de Fst y Nm calculados para las poblaciones de Triatoma venosa mediante el programa RAPDFST
El análisis de los datos con el programa RAPDDIST permitió generar un dendrograma para las dos poblaciones evaluadas (Fig. 4). En este dendrograma no se observa una diferenciación genética entre la población doméstica y peridoméstica con respecto a los individuos utilizados como grupo de exclusión, dado que el cluster que agrupa a las dos primeras presenta la misma distancia genética, indicando de esta manera la poca diferenciación genética encontrada entre las poblaciones evaluadas de T. venosa en este estudio.
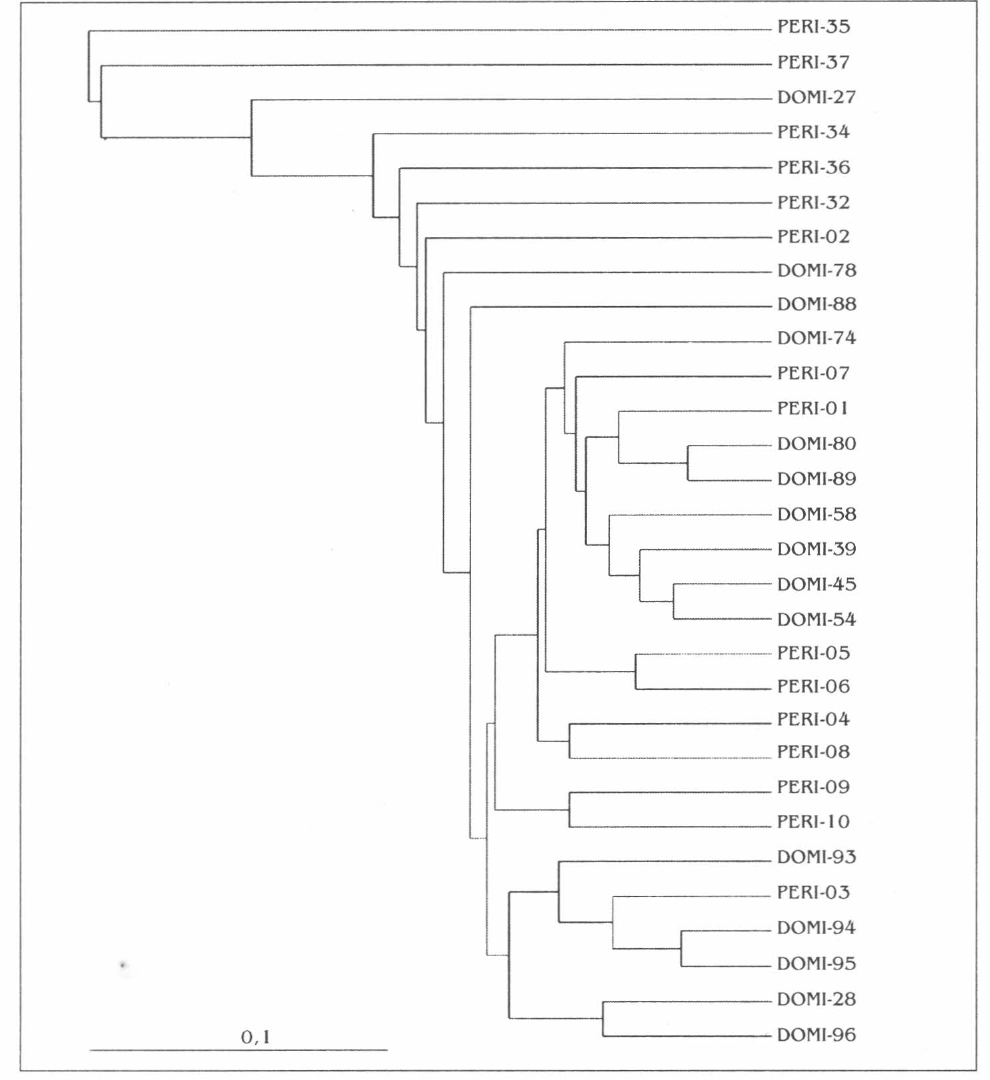
Dendrograma de los individuos de las poblaciones doméstica (DOMI) y peridoméstica (PERI) de Triatoma venosa generado con RAPDPLOT, y el método UPGMA, para 70 loci.
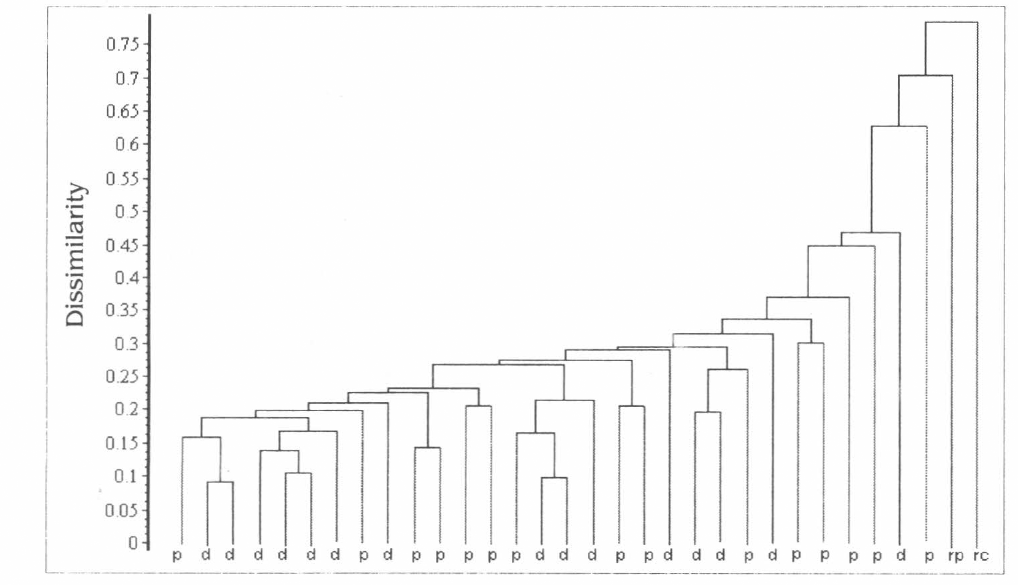
Dendrograma generado con SYNTAX 2000, a partir de 70 marcadores RAPD con los iniciadores 2, 3, 4 y 5 para individuos de Triatoma venosa peridomésticos (p) y domésticos (d). Se utilizó un individuo Rhodnius prolixus (rp) y un individuo Rhodnius colombiensis (rc) como grupos de exclusión.
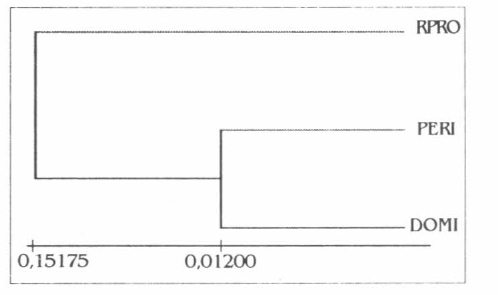
Dendrograma generado con el programa RAPDIST de la distancia genética de Nei y Li (1972), entre las poblaciones peridoméstica y doméstica de Triatoma venosa, empleando el método UPGMA y 1.000 repeticiones. Se empleó Rhodnius prolixus como grupo de exclusión.
Discusión
Los resultados obtenidos a partir de los marcadores moleculares RAPD proveen una base molecular para evaluar las relaciones genéticas entre los triatominos (García et al. 1998). Esta técnica se ha utilizado ampliamente para analizar el genoma de otros insectos vectores como el vector de la malaria Anopheles gambiae (Favia et al. 1994), o para identificar poblaciones de Aedes albopictus (Kambhapati et al. 1992). Jaramillo et al. (2001), mediante RAPD, encontraron diferencias entre Rhodnius prolixus y R. colombiensis lo que llevó a proponer que el control de poblaciones domésticas de Rhodnius no se verían influenciadas de manera importante por invasiones silvestres (Guhl y Schofield 1996).
Con los resultados preliminares obtenidos entre las poblaciones de T. venosa se sugiere que ocurre un elevado flujo genético entre las mismas, debido a que agrupan en la misma rama del dendrograma (Fig. 4), diferente a lo observado para Rhodnius prolixus (de carácter domiciliado) y R. colombiensis utilizados como grupos de exclusión en este estudio (Fig. 3), los cuales no presentan flujo genético entre sí (Jaramillo et al. 2001).
Adicionalmente, T. venosa, aparentemente presenta un flujo genético mayor que el indicado para otras especies como Rhodnius (Jaramillo et al. 2001), T. dimidiata (Jaramillo et al. 2003), o para mariposas como Papilo glaucus en Ohio, Georgia y Florida donde se registró un Nm de 0,0032 (Bossart y Scriber 1995).
Los valores de Nm obtenidos para T. venosa indican una migración significativa de individuos por generación o un potencial de dispersión suficiente para mantener homogeneidad genética, debido a que son mayores a 1, lo que hace que las frecuencias alélicas permanezcan homogéneas en las poblaciones (Wright 1931). Con los resultados se observa que hay migración de por lo menos 4,2 insectos por generación entre las poblaciones (Tabla 2), lo que contribuiría a mantener homogeneidad genética y a hacer más difícil el control de este vector en la transmisión de la enfermedad de Chagas, en el caso que T. venosa se encontrara como un vector eficiente de la transmisión del parásito.
Los valores de Fst obtenidos (Tabla 2), indican que hay poca diferenciación entre las poblaciones de T. venosa; es decir, que hay un intercambio genético entre las poblaciones evaluadas.
Estos hallazgos son similares a los encontrados para T. dimidiata (Jaramillo et al. 2003), debido a que las poblaciones no domiciliadas de T. venosa, al igual que las poblaciones no domiciliadas de T. dimidiata, estarían representando un riesgo epidemiológico en la transmisión de la enfermedad de Chagas.
Dentro del marco del programa nacional de control y eliminación de la enfermedad de Chagas en Colombia, estudios como éste contribuyen en el entendimiento del comportamiento de especies de triatominos de importancia secundaria que pueden tener la capacidad de invadir viviendas rurales, siguiendo de esta manera las recomendaciones hechas por Schofield et al. (1999).
La relevancia de T. venosa en la transmisión de la enfermedad de Chagas es desconocida hasta el momento, ya que no hay estudios que indiquen una tasa de infección por tripanosomas, pero, dado el elevado flujo genético que sugieren los resultados de este estudio preliminar, podría ser un vector potencial de difícil control.
Conclusiones
Con el número de individuos evaluados, no se encuentra una divergencia genética elevada entre las poblaciones de T. venosa.
Mediante la técnica de RAPD no se obtuvieron patrones de bandeo que permitieran diferenciar las poblaciones doméstica y peridoméstica de T. venosa.
El índice de fijación (Fst) y la tasa efectiva de migración (Nm) estimados, sugieren un flujo genético suficiente para mantener una homogeneidad genética entre las poblaciones.
Existe flujo de genes entre las poblaciones domiciliadas y peridomiciliadas estudiadas de T. venosa
El movimiento de los insectos entre las poblaciones estudiadas hace necesario un mayor control del peridomicilio en los programas de eliminación de insectos vectores de la enfermedad de Chagas.
Aunque hasta el momento se desconoce la capacidad vectorial de T. venosa, el posible flujo genético encontrado puede ser un factor determinante para el aumento de su capacidad vectorial.
Footnotes
Agradecimientos
Este proyecto se llevó a cabo gracias al apoyo financiero de Colciencias proyecto Cód: 1204-04-13018 y la Facultad de Ciencias de la Universidad de los Andes.
