Abstract
Starch gel electrophoresis was used to elucidate genetic variation at 12 isoenzyme loci among six allopatric Colombian populations of the cluster martensis (D. martensis, D. starmeri and D. uniseta), from Santa Marta (Magdalena Department), Camarones (Guajira Department) and from the Tatacoa desert (Huila Department). This estimation was compared to a phylogenetically related (D. buzzatii) and distant (D. melanogaster) species. The enzymatic divergences were inferred from genetic distances and the results allowed the identification of six levels of taxonomic divergence: Local population (D = 0,1031), subraces (
Introducción
El subgénero Drosophila se originó en la zona tropical del viejo mundo. La radiación inicial para los linajes del nuevo mundo surgieron a partir de la rama ancestral virilis/ repleta. Uno de los linajes más conspicuos y que ha presentado sucesivas radiaciones de Drosophila es el grupo repleta. La característica más notable de este grupo es que las especies utilizan como nicho trófico los cactus en descomposición, condición que le ha permitido establecerse en ambos hemisferios en zonas templadas, desérticas y semiáridas de los trópicos y semi - trópicos (Wasserman 1962; Sánchez 1987; Powell 1997; Castañeda 2000).
Las 89 especies del grupo repleta se caracterizan por poseer una cerda en cada punto negro del mesonotum, aspecto que las distingue de los otros. Los estudios morfológicos y citogenéticos han permitido dividirlo en seis subgrupos o complejos: repleta, mercatorum, hydei, mulleri, fasciola y buzzatii (Patterson y Stone 1952; Wasserman 1962, 1967; Ruiz y Wasserman 1993). El subgrupo buzzatii está compuesto por los enjambres o clusters stalkeri, buzzatii y martensis. El enjambre martensis está conformado por las especies: D. martensis (Wasserman, Wilson en Vilela 1983), D. uniseta (Wasserman; Koepfer; Ward en Vilela 1983), D. starmeri (Wasserman, Koepfer, Ward en Vilela 1983) y D. venezolana (Ruiz y Fontdevila 1981).
Las especies del enjambre martensis son sinmórficas y están estrechamente relacionadas, porque comparten una serie de inversiones que les son únicas (Xabcj, 2abmnz7, 5d2). Su ancestro debió presentar un alto polimorfismo, que ha evolucionado a D. starmeri. Las demás emergieron de éste fijando sus propias inversiones; muchas de las cuales han permanecido polimórficas en D. starmeri (Wasserman 1962; Ruiz y Wasserman 1993; de Polanco 1998; Prada 2002).
Estas especies se encuentran distribuidas en las zonas semiáridas del norte de Sudamérica (Colombia, Venezuela y Antillas holandesas). Se conoce que ocupan recursos diferenciados (Benado et al. 1984). D. uniseta utiliza exclusivamente el cactus columnar Ritterocereus griseus. D. martensis emerge tanto de los columnares como de opuntias; D. starmeri prefiere los columnares y ocasionalmente explota los opuntias (Ruiz y Fontdevila 1981; Sánchez 1987).
En Colombia estas especies han sido detectadas en los departamentos de la Guajira, Magdalena, César y Cundinamarca (Ruiz y Fontdevila 1981; Sánchez 1987; Hoenigsberg et al. 1987). En el Huila se coleccionaron por primera vez en el desierto de la Tatacoa, por de Polanco (1998).
En el ámbito reproductivo, Rojas (2001) confirma que todas las especies del enjambre martensis se comportan como verdaderas. Las poblaciones geográficamente aisladas de la costa norte y el desierto de la Tatacoa tanto en D. starmeri como en D. martensis, han manifestado divergencias significativas a nivel morfológico y reproductivo (Castañeda 2000; Rojas 2001). En la especie D. starmeri la población de Santa Marta presenta mayor polimorfismo cromosómico que las poblaciones de Camarones y Rosalía (Prada 2002). Desafortunadamente en D. uniseta no se han realizado estudios comparativos entre las poblaciones de estas dos localidades.
Sin embargo, no se tiene ningún conocimiento sobre la diferenciación enzimática que presentan estas poblaciones alopátricas. En este estudio se pretendió llenar este vacío utilizando geles de almidón para inferir, en doce loci, el grado de divergencia alozímica existente entre ellas, con la intención de aportar evidencia molecular que pueda ser utilizada para descifrar su estado evolutivo.
Materiales y Métodos
Muestras
Se estudiaron tres especies del enjambre martensis (D. martensis, D. starmeri y D. uniseta), una relacionada a este enjambre, D. buzzatii y otra filogenéticamente más distante, D. melanogaster. El número de individuos promedio utilizado por especie fue de 18, coleccionados desde 1998 en las poblaciones de Santa Marta y Camarones (costa norte) y en Rosalía (vereda el “Cuzco”, desierto de la Tatacoa). La población de D. melanogaster proviene de una colección realizada en el año 2001, en la localidad de Rosalía. D. buzzatii es una cepa procedente del laboratorio de genética de la Universidad de Barcelona (España) que ha sido mantenida en el Instituto de Genética, de la Universidad de Los Andes desde el año 1996.
Análisis isoenzimático
Análisis genético
Las frecuencias alélicas, heterocigosidad, la distancia genética e Identidad Genética de Nei (1978, 1987), se calcularon con el programa PopGene versión 1.31 (Yeh et al. 1999). Las relaciones filogenéticas entre los grupos estudiados se establecieron a través del dendograma construido por este programa, que emplea el algoritmo UPGMA. Además, se calcularon los siguientes parámetros:
el porcentaje de bandas comunes o de similitud ( la frecuencia de alelos comunes ( el error estándar asociado a la distancia genética de Nei (ES =[(1-I)/In)]1/2, Zouros 1973).
Resultados y Discusión
Variabilidad enzimática en las especies analizadas
En la tabla 1 se aprecian las frecuencias alélicas de los sistemas analizados los cuales fueron todos polimórficos. Los sistemas enzimáticos que presentaron mayor número de alelos, en el enjambre martensis, son la PGD (10 alelos) y a EST (8 alelos). D. martensis y D. uniseta exhibieron mayor variabilidad en el sistema MDH y D. starmeri en PGD.
Variación alélica de 12 sistemas enzimáticos en 8 poblaciones
Los valores de heterocigosidad de los loci analizados difieren significativamente de los esperados en todas las poblaciones analizadas del enjambre martensis, excepto para las enzimas Isocitrato deshidrogenasa (D. starmeri Santa Marta, X2= 5,48; df = 3; P< 0,05) y Malato deshidrogenasa (D. uniseta - Rosalía, X2= 3,31; df= 1; P<0,05). Los valores de heterocigosidad promedio observada para cada sistema son una tercera parte del valor esperado en todas las poblaciones estudiadas (Tabla 2). Aunque este fenómeno es típico en muchas especies de Drosophila (Ayala y Tracey 1974; Sánchez 1987), se debe tener en cuenta que el número de individuos es relativamente bajo (X = 18) y que no han sido recientemente coleccionados, por tanto, en el laboratorio estas poblaciones han podido sufrir sucesivos cuellos de botella.
Número de alelos muestreados (N), alelos promedio por locus (G) y heterocigosidad promedio observada y esperada (Ho y He) en poblaciones del enjambre martensis examinadas para 12 sistemas enzimáticos (error estándar en paréntesis)
Las especies del enjambre martensis presentaron un valor medio de alelos por locus de 3,2 y una heterocigosidad media de 0,1804. El valor medio más alto de alelos por locus lo manifestó D. starmeri (3,8) y el más bajo lo mostró D. uniseta con 2,4 (Tabla 2). Las poblaciones de D. martensis presentan, en general, valores de variabilidad análogos a los de las poblaciones de D. starmeri y también mayores que los de D. uniseta (especie monófoga). En cierta manera este resultado puede estar reflejando la especificidad de nicho que presenta D. uniseta, en contraste con D. starmeri y D. martensis que son especies polífogas (Barker y Mulley 1976); quizás esta diferenciación enzimática sea una insinuación de la importancia del sustrato utilizado por cada una de las especies.
Las poblaciones de D. starmeri de la costa norte (Santa Marta y Camarones) presentaron un valor medio de heterocigosidad mayor (0,1988) que la población de Rosalía en el desierto de la Tatacoa (0,1250). En la especie de D. martensis se observó lo contrario, un valor de heterocigosidad mayor en la población de Rosalía que en la población de Santa Marta. Estos resultados reflejan parte de la diferenciación genética que existe entre estas poblaciones alopátricas.
Niveles de identidad intra e inter específico
Distancias genéticas con sus respectivos errores estándar (bajo la diagonal) y las dentidades genéticas (sobre la diagonal) obtenidas para 12 loci enzimáticos
1= D. buzzatii, 2= D. melanogaster, 3 D. starmeri - Rosalía, 4= D. starmeri-Santa Marta, 5= D. starmeri-Camarones, 6= D. martensis-Rosalía, 7 D. martensis-Santa Marta y 8 D. uniseta-Rosalía
Las comparaciones entre las especies del enjambre martensis (D. martensis, D. starmeri y D. uniseta) aún cuando son morfológicamente similares, dieron un buen índice de divergencia genética entre ellas (10,4559), el cual se reduce a 0,3682 cuando se comparan especies de enjambres diferentes (D. buzzatii vs. especies del enjambre martensis) y como es esperado, la identidad más baja se da entre las especies morfológicamente más diferenciadas 0,2462 (D. melanogaster us. las demás). Los valores de identidad genética entre las poblaciones se pueden observar más fácilmente en la figura 1. En donde se destaca, en color negro, el valor de la identidad genética en las poblaciones de la costa norte y en gris las poblaciones de las distintas zonas geográficas para las especies de D. martensis y D. starmeri.
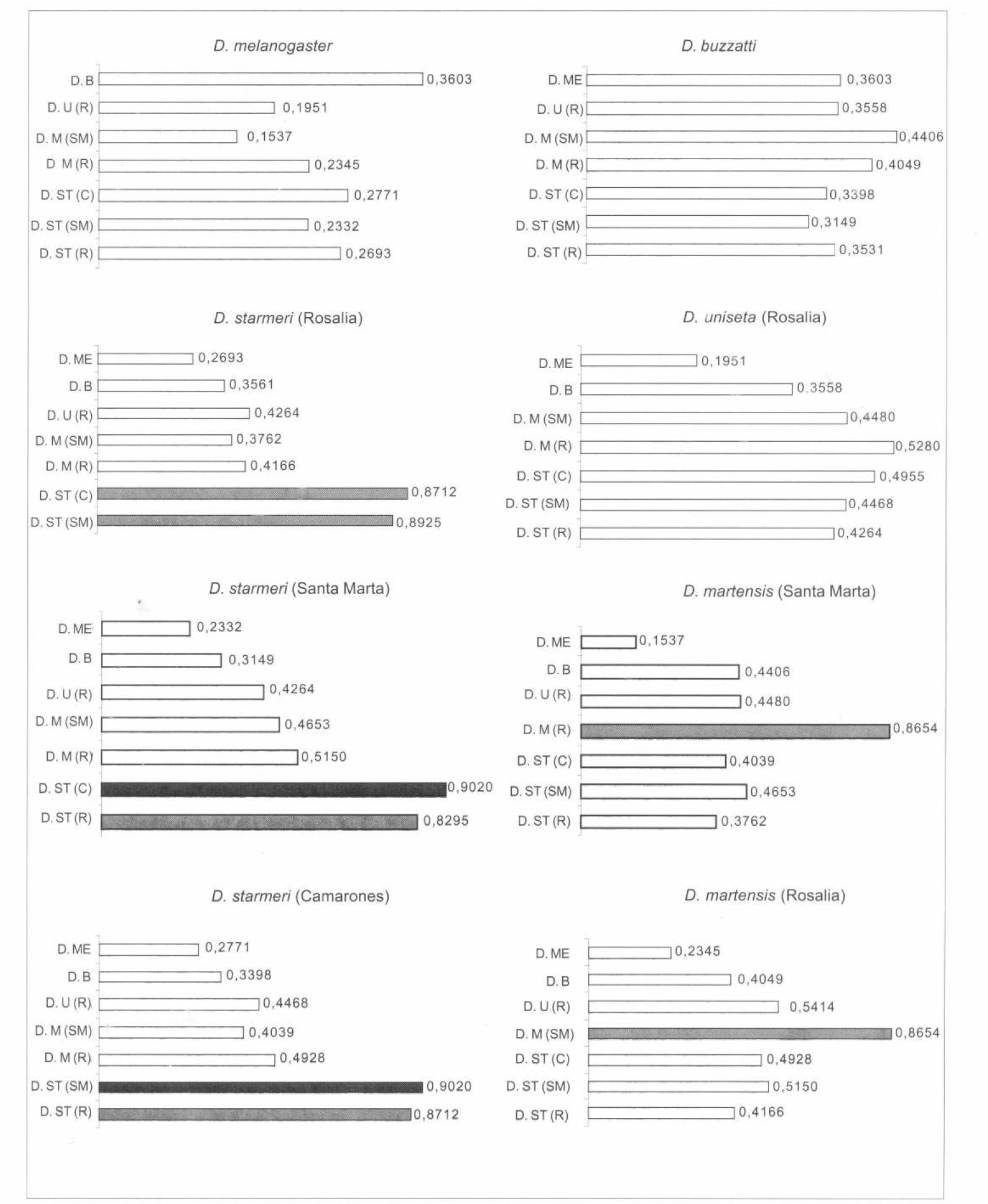
Distribución de Identidades entre las diferentes especies estudiadas para 12 sistemas enzimáticos. D. B. = D. buzzatii, D. ST (R) = D. starmeri (Rosalía), D. ST (C) = D. starmeri (Camarones), D. ST (SM) = D. starmeri (Santa Marta), D. M (R) = D. martensis (Rosalía), D. M (SM) = D. martensis (Santa Marta), D. U (R) = D. uniseta (Rosalía)
Porcentaje de similitud (S)
Los porcentajes promedios de bandas comunes o de similitud entre las poblaciones estudiadas se calcularon utilizando la ecuación de Nair et al. (1971). Al comparar todas las poblaciones geográficamente aisladas de D. starmeri y D. martensis se encontró que solo comparten un 78,9% de bandas comunes, denotando que son unidades diferentes. Detallando las diferencias por especie se observó que S decrece de la siguiente manera: 84,44%, entre las poblaciones de Santa Marta y Rosalía (D. martensis), 83,33% entre las poblaciones de Santa Marta y Camarones (D. starmeri), 76,09% entre Santa Marta y Rosalía (D. starmeri) y 71,74% entre Camarones y Rosalía(D. starmeri).
Los resultados también permitieron observar que el valor de similitud, como es lógico, disminuye de acuerdo con el nivel evolutivo: 35,75% al comparar especies del mismo enjambre, 23,18% especies de diferentes enjambres y 17,31% especies de grupos diferentes. De manera coherente, los porcentajes de S se aproximan a los valores obtenidos de las identidades genéticas.
Niveles de diferenciación genética intra e inter específica
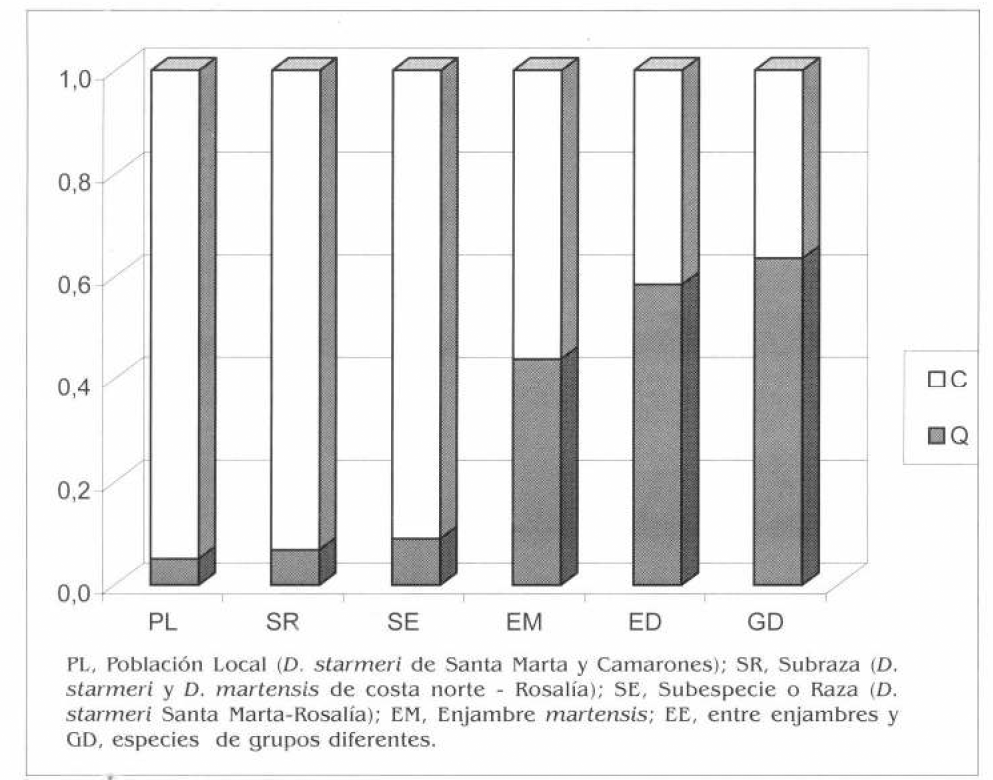
Comparación de frecuencias alélicas promedio de alelos no comunes (Q) y comunes (C). PL, Población Local (D. starmeri de Santa Marta y Camarones); SR, Subraza (D. starmeri y D. martensis de costa norte Rosalía); SE, Subespecie o Raza (D. starmeri Santa Marta-Rosalía); EM, Enjambre martensis; EE, entre enjambres y GD, especies de grupos diferentes.
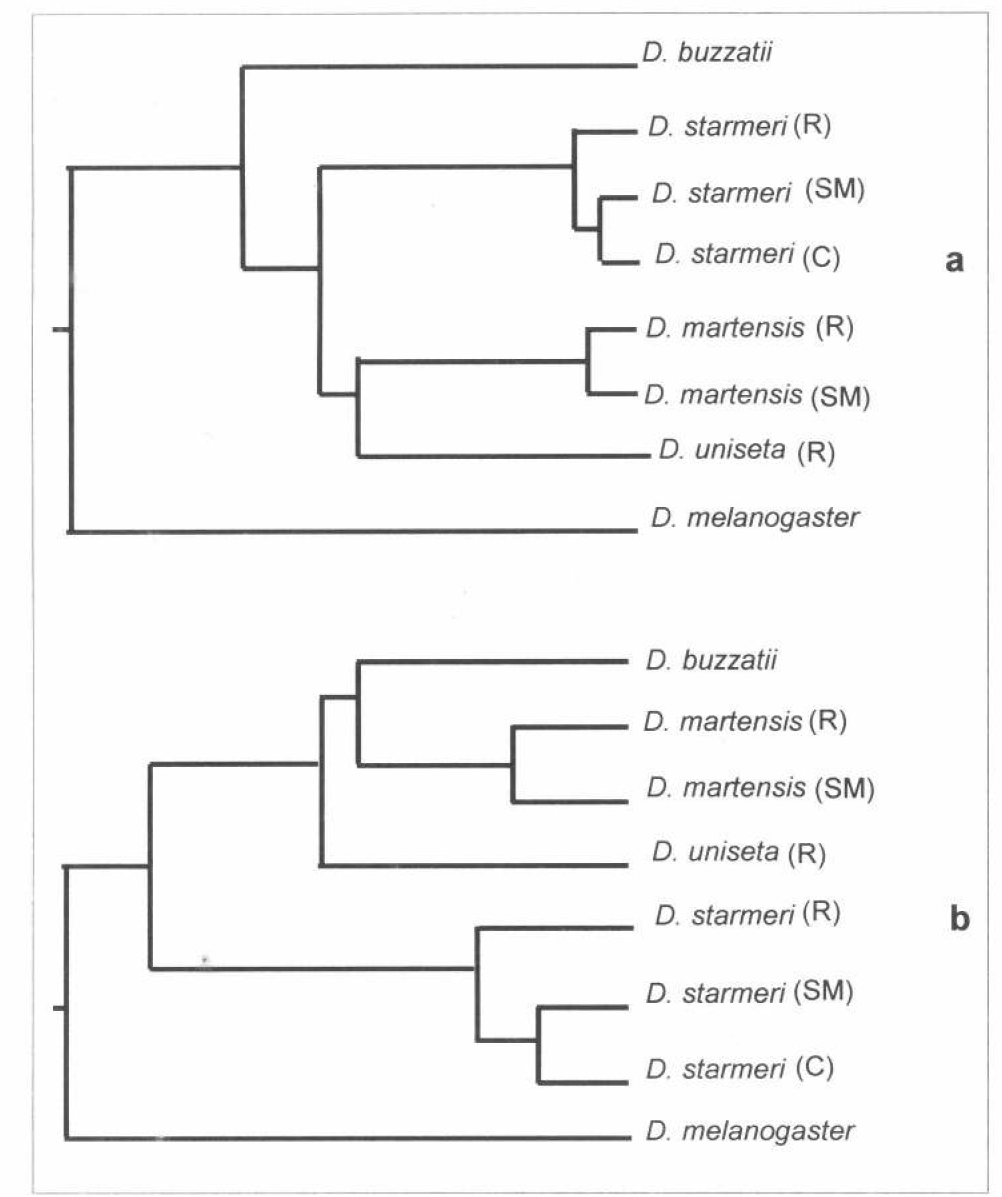
Fenograma obtenido por el método de UPGMA usando la Distancia (D) de Nei (1978). a, incluye todos los doce loci analizados. b, excluye los loci ubicados en del segundo cromosoma (R) = Rosalía, (SM) = Santa Marta, (C) = Camarones
Dendograma
En la topología del árbol generado, se evidencia el valor sistemático de los resultados electroforéticos, los cuales permiten separar claramente las distintas especies. Por un lado el enjambre martensis aparece relacionado con la especie evolutivamente más cercana, D. buzzatii y como la más distante del grupo surge D. melanogaster. Las especies del enjambre martensis se pueden diferenciar visiblemente en dos grupos, uno reúne las poblaciones de D. starmeri y otro está conformado por D. martensis y D. uniseta. Además, es apreciable la separación en el árbol, entre las poblaciones de la costa norte y el desierto de la Tatacoa, tanto para D. martensis como D. starmeri. Contrariamente, las poblaciones de Santa Marta y Camarones (costa norte) en D. starmeri aparecen agrupadas (Fig. 3 a).
Las relaciones evolutivas insinuadas anteriormente podrían ser desvirtuadas sí la tasa de cambio evolutivo, a la cual se ha dado la alta variabilidad observada en el segundo cromosoma de estas especies, no es constante (Sánchez 1987; Beltrán et al. 1995; de Polanco 1998). Por tal motivo se realizó un fenograma excluyendo los loci ubicados en este cromosoma (Fig. 3 b). La topología del árbol generado cambió la relación de D. buzzatii agrupándola con las especies del enjambre martensis y relacionándola más con D. martensis, y no con D. starmeri como se observó al incluir todos los loci (Fig. 3 a). Vale la pena destacar que las relaciones de las poblaciones alopátricas no se alteran ni en D. starmeri ni en D. martensis. Este resultado insinúa que los loci que determinan estas diferencias también se encuentran en otros cromosomas.
Los altos valores de errores estándar de las distancias genéticas pueden estar asociados tanto al número bajo de muestreo como de loci analizados. El análisis de las divergencias genéticas de las poblaciones alopátricas en estudio se confrontó con la información de diferenciación a nivel morfométrico, reproductivo y citogenético, que éstas han manifestado (de Polanco 1998; Castañeda 2000; Rojas 2001; Prada 2002). Con la matriz de distancia genética de Nei se sugieren los siguientes seis niveles de diferenciación, que se ajustaron al grado de divergencia taxonómica (Tabla 3).
Población local
El par de poblaciones Santa Marta y Camarones (costa norte), en la especie D. starmeri exhibió una distancia genética propia de poblaciones locales (D = 0,1031). Aunque es ligeramente superior a la informada por Sánchez (1987) para las poblaciones locales venezolanas de la misma especie (D = 0,069). Esta diferencia puede ser un reflejo de procesos ecológicos propios de cada localidad. Castañeda (2000) comprobó que las poblaciones de la costa norte tienen su propia estructura morfométrica, pero conservan su identidad como especie.
Subrazas
En D. starmeri y D. martensis las comparaciones entre las poblaciones de la costa norte y el desierto de la Tatacoa mostraron un valor promedio de distancia genética de 0,1412 ± 0,002. Es decir, se han acumulado en el tiempo 14 sustituciones alélicas por cada cien loci; valor que es 1,4 veces superior a la divergencia manifestada en D. starmeri en las poblaciones locales de la costa norte. Esta divergencia es mayor en D. martensis (0,1446) que en D. starmeri (0,1379). La magnitud de esta divergencia cae dentro del intervalo encontrado para subespecies por otros autores (Ayala et al. 1972; Zouros 1973; Sánchez 1987). Sin embargo, cuando se comparan los promedios de las frecuencias de alelos no comunes, se observa que tales poblaciones (Q =0,0679), no difieren sustancialmente de lo detectado en D. starmeri para poblaciones locales (Q = 0,0509). Zouros (1973) tampoco encontró diferencias entre las poblaciones locales (0,0016) y subrazas (0,002) del grupo mulleri. Por lo tanto, se considera que las poblaciones de D. starmeri y D. martensis de estas zonas alopátricas posiblemente presentan una divergencia típica de subrazas.
Entre las poblaciones de la costa norte y el desierto de la Tatacoa de las especies anteriormente mencionadas, también se ha evidenciado diferenciación a otros niveles. Rojas (2001), al realizar cruces circulares entre las poblaciones de Santa Marta, Camarones y Rosalía, observó que la viabilidad de los híbridos de la F1 (en las dos vías) y la descendencia de los retrocruces disminuyó significativamente tanto en D. starmeri como en D. martensis, siendo este efecto más acentuado en esta última especie; sin embargo, esta diferenciación no se reflejó a nivel alozímico para D. martensis. No obstante para poder inferir adecuadamente al respecto es necesario analizar un mayor número de loci y de individuos. Además, Castañeda (2000) entre las poblaciones de D. starmeri de estas dos zonas geográficas evidenció que son morfológicamente diferentes (D. mahalanobis = 13,383).
Subespecie o raza
El valor de distancia genética más alto entre estas poblaciones alopátricas se detectó en D. starmeri, para las poblaciones de Santa Marta y Rosalía (0,1870). El cual es análogo al informado por otros autores para la categoría de subespecie (Hubby y Throckmorton 1965; Ayala et al. 1972; Yang et al. 1972; Zouros 1973; Sánchez 1987). Es decir, han ocurrido aproximadamente 19 sustituciones alélicas, acumuladas en el tiempo, por cada 100 loci entre estas poblaciones; divergencia que es aproximadamente 2,8 veces más grande que la distancia que exhibieron las poblaciones locales venezolanas, de la misma especie y 1,8 más grande que la población local de la costa norte.
Estas poblaciones manifestaron una reducción significativa de la descendencia en la F1 (Rojas 2001). En la población de Santa Marta, Prada (2002) observó un mayor polimorfismo y la presencia de heterocariotipos en híbridos cuando realizó cruces entre esta población y Rosalía. Además, Castañeda (2000) determinó morfométricamente, mediante distancias de Mahalanobis, que son diferentes (D.M. = 14,021). Aunque a nivel de aislamiento precigótico de selección múltiple, Pérez (2002) no encontró diferencias significativas entre estas poblaciones, sí se manifestó una tendencia hacia el reconocimiento de individuos de una misma localidad. Se denota que el aislamiento reproductor entre estas poblaciones es aún insuficiente, pero que ha comenzado a insinuarse. Por lo anteriormente mencionado se podría sugerir que dichas poblaciones están iniciando la primera etapa de especiación.
Enjambre martensis
Las distancias genéticas entre las especies del enjambre martensis (D. martensis, D. starmeri y D. uniseta) exhibieron valores que oscilan entre 0,6387 y 0,9777, con un valor medio de D=0,7907±0,0315. Sánchez (1987), para estas mismas especies, analizando 22 sistemas enzimáticos, encontró valores de divergencia que fluctúan entre 0,647 y 0,840, con un valor medio de 0,7225. Este nivel de diferenciación cae dentro del intervalo de distribución observado en otros enjambres de grupos diferentes (Ayala y Tracey 1974; Eisses et al. 1979; Cabrera et al. 1980; Cabrera et al. 1983).
Enjambres o clusters diferentes
El nivel de divergencia genética entre las poblaciones del enjambre martensis y D. buzzatii (D=1,0055±0,0366), se incrementó con respecto a lo obtenido para el enjambre martensis. Este resultado es concordante con los referenciados por Ayala y Tracey (1974) y Eisses et al. (1979) para enjambres del grupo willistoni y melanogaster.
Especies de grupos diferentes
La divergencia genética entre especies de grupos diferentes, como es lógico, manifiesta los valores más altos de distancia genética (Cabrera et al. 1980; Cabrera et al. 1983). Hecho que se confirmó en este estudio al comparar D. melanogaster con las poblaciones de D. martensis, D. starmeri, D. uniseta, y D. buzzatii, las cuales presentaron un valor medio de 1,4327 ± 0,0934.
En la figura 4 se grafican las identidades y distancias entre los diferentes niveles taxonómicos detectados. Se aprecia un incremento gradual, desde el nivel de población local hasta el nivel de especies completamente diferenciadas. Las comparaciones entre las frecuencias de alelos comunes (C) y no comunes (Q), en los distintos niveles taxonómicos, se ajusta a lo encontrado por Zouros (1973) en especies del enjambre mulleri. En la figura 2 se muestra la relación inversa de Q y C para los diferentes niveles de divergencia.
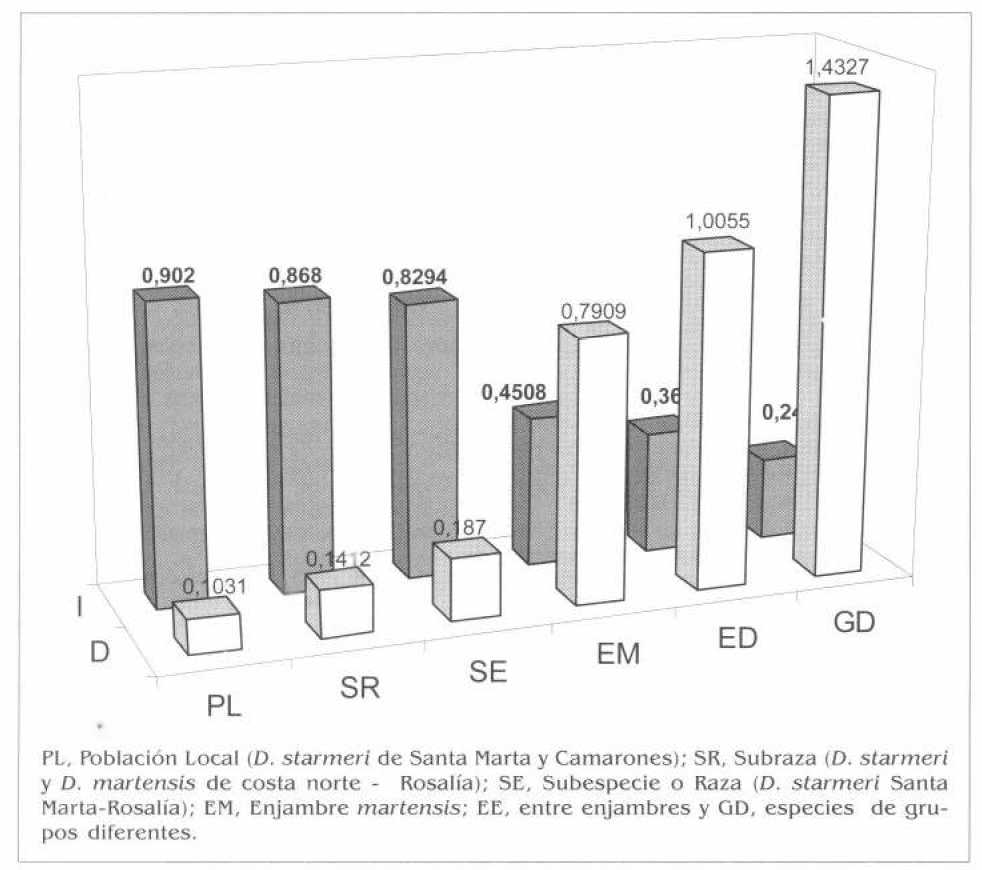
Comparación de identidades genéticas (I) y distancias genéticas (D) para todos los niveles de divergencia taxonómicos. PL, Población Local (D. starmeri de Santa Marta y Camarones); SR, Subraza (D. starmeri y D. martensis de costa norte Rosalía); SE, Subespecie o Raza (D. starmeri Santa Marta-Rosalía); EM, Enjambre martensis; EE, entre enjambres y GD, especies de grupos diferentes.
En la figura 5 se grafican todos los parámetros analizados en este estudio para las especies del enjambre martensis, en la cual se puede apreciar que D. starmeri fue la especie más divergente. En esta especie el par de poblaciones Rosalía - Santa Marta (R-SM) presenta mayor diferenciación respecto al par de poblaciones locales, de Santa Marta y Camarones (SM-C).
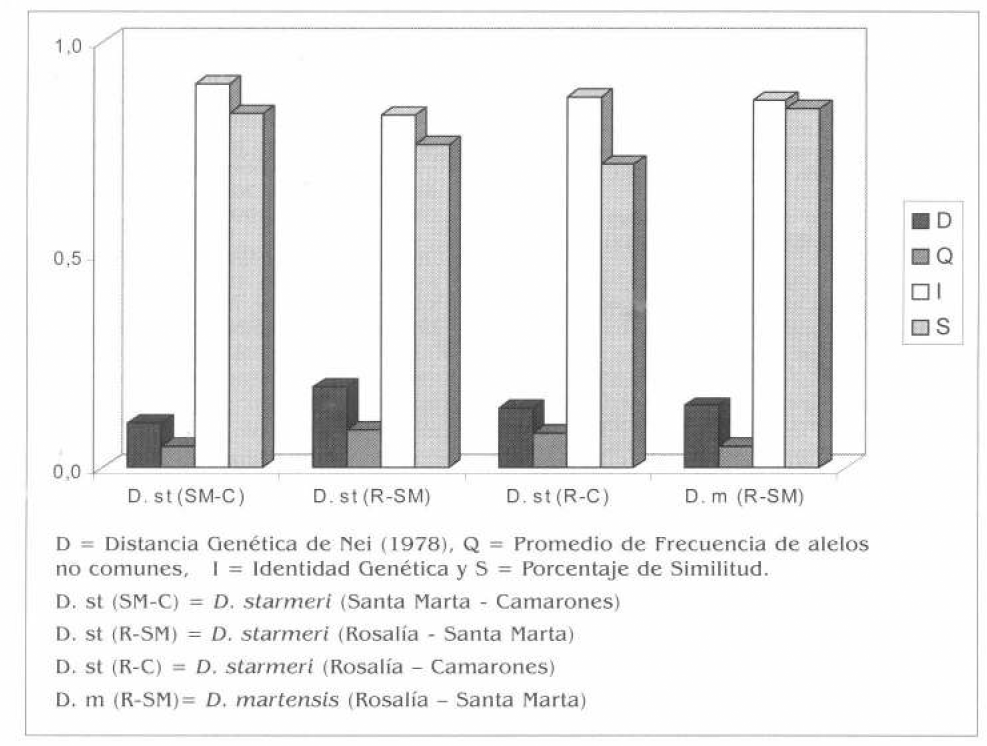
Comparación de parámetros para las poblaciones del enjambre martensis. D = Distancia Genética de Nei (1978), Q = Promedio de Frecuencia de alelos no comunes, I = Identidad Genética y S = Porcentaje de Similitud. D. st (SM-C) = D. starmeri (Santa Marta Camarones). D. st (R-SM) = D. starmeri (Rosalía Santa Marta). D. st (R-C) = D. starmeri (Rosalía Camarones). D. m (R-SM)= D. martensis (Rosalía - Santa Marta)
Conclusiones
Las especies del enjambre martensis (D. martensis, D. starmeri y D. uniseta) exhibieron bajos valores de heterocigosidad, fenómeno ya evidenciado en otras especies cactofílicas del grupo repleta.
El análisis de los doce loci enzimáticos permitió sugerir seis niveles de divergencia taxonómica entre las especies: Población local (D = 0,1031), subrazas (D = 0,1412), subespecies o razas (D = 0,1870), especies de un mismo enjambre o cluster (= 0,7907), especies de enjambres diferentes (D = 1,0055) y especies de grupos diferentes (D = 1,4327).
El dendograma construido, a partir de la matriz de distancias genéticas, separó acertadamente las especies analizadas de acuerdo con su divergencia evolutiva.
Con esta investigación se pudo establecer que en D. starmeri las poblaciones geográficamente más cercanas (costa norte) no se diferenciaron alozímicamente, mientras que las poblaciones más distantes (costa norte y desierto de la Tatacoa) tanto en D. starmeri como en D. martensis, son diferentes alozímicamente. La divergencia más contundente se manifestó en D. starmeri entre las poblaciones de Santa Marta y Rosalía. Así en este estudio preliminar se sugiere un posible ejemplo de especiación alopátrica incipiente.
Recomendaciones
Realizar un análisis más riguroso ampliando tanto el número de individuos (los cuales deben ser recién coleccionados) como el número de loci analizados (mínimo 24), para evaluar el estado real evolutivo de las especies objeto de estudio.
Confrontar el grado de diferenciación genética obtenido a partir de las distancias genéticas de Nei, en este estudio, con otros métodos igualmente potentes como distancia de Mahalanobis y transformaciones angulares como las de Cavalli-Sforza y Eduarws.
Extender los estudios morfométricos, cromosómicos, de cortejo y selección múltiple en las poblaciones colombianas de D. martensis y D. uniseta.
Footnotes
Agradecimientos
Se agradece a los profesores Gonzalo Palomino y Francisco Villa que colaboraron en las salidas de campo y a los estudiantes de biología de la Universidad del Tolima, por la ayuda en el muestreo que permitió obtener los individuos objeto de estudio. Al Director del Instituto de Genética, Mauricio Linares, por permitir realizar esta investigación en el laboratorio de electroforesis de la Universidad de los Andes. A la secretaria del Instituto de Genética, Cielo Rocío de Oro por su asistencia incondicional. A los comités de investigaciones de la Universidad de los Andes (Decanatura de Ciencias - Investigaciones varias, centro de costo 280) y de la Universidad del Tolima (465) por sus aportes económicos para la realización de este proyecto.
