Abstract
Recent investigations have been suggested mitochondrial DNA as important tool in molecular entomology studies that include not only species identification, but also establishment of phylogenetic and evolutive relationships among insects.
In this work we amplified and sequenced a fragment of 380 pb from the mitochondrial ribosomal large subunit; this preliminary work was done in order to obtain sequences with potential use as taxonomic character in sand flies. Primers used for PCR amplification and DNA sequencing were designed based on the consensus sequence of insects previously reported for this region. A bias toward adenine and thymine (81%) is consistent with the base composition of mtDNA sequences of other insects. Multiple alignment among sequences did not show ambiguities characteristic of nuclear DNA and preliminary comparisons suggest their utility as taxonomic character at the species level.
Introducción
Los flebotomineos, (Diptera:Psychodidae) de los géneros
Los estudios epidemiológicos y de control de la enfermedad requieren la identificación de la o las especies vectoras; sin embargo, este trabajo, basado generalmente en caracteres morfológicos, se dificulta por el pequeño tamaño de estos insectos y los procedimientos necesarios para la observación de estructuras internas importantes como las espermatecas de las hembras, que requieren aclaración y montaje de los especímenes. Adicionalmente, muchos de los caracteres morfológicos diagnósticos de especie se encuentran presentes en un solo sexo (Young y Duncan 1994).
La existencia de especies isomórficas y complejos de especies en flebotomineos ha sido sugerida mediante estudios isoenzimáticos y por algunas técnicas de entomología molecular como amplificación al azar de fragmentos de ADN usando PCR (Lanzaro y Warburg 1995); tales estudios han señalado la necesidad de implemetar nuevas estrategias que permitan identificar las especies que conforman los complejos y que podrían diferir en aspectos como la capacidad vectorial, lo cual traería importantes implicaciones en la transmisión de la enfermedad (Lanzaro y Warburg 1995).
Así mismo y de acuerdo con los principales estudiosos de la taxonomía de estos pequeños dípteros de la familia Psychodidae, los esque mas de clasificación y la interpretación de los mismos deben ser constantemente reexaminados y la inclusión de nuevos caracteres taxonómicos -además de los morfológicos- es necesaria para la determinación de las relaciones taxonómicas y filogenéticas, un aspecto poco estudiado y entendido hasta ahora (Young y Duncan 1994).
El ADN mitocondrial, por su herencia materna y su relativa tasa de cambio rápida, se constituye en una herramienta importante de la entomología molecular que permite su utilización en estudios taxonómicos aumentando el número de caracteres disponibles para tales estudios y solucionando dificultades de la taxonomía clásica (Beard
En el presente estudio se amplificó y secuenció exitosamente un fragmento de 380 pb obtenido a partir de
Materiales y Métodos
Especímenes de Lutzomyia spp.
Las secuencias fueron obtenidas de 18 especímenes de
Los especímenes estudiados de
Procedencia de los especímes de Lutzomyia spp. utilizados para la extracción y ampliación de ADN
Aislamiento y amplificación de ADN por técnicas de PCR.
Los especímenes fueron criopreservados o mantenidos en isopropanol al 100%. Para la extracción de ADN solo se utilizaron machos cuyas terminalias fueron previamente removidas y aclaradas en medio Hoyer's para verificar la identidad de la especie usando las claves taxonómicas de Young y Duncan (1994). El ADN fué aislado de especímenes individuales por el método de Collins y Porter (1990); tres especímenes se utilizaron por cada localidad para L. longipalpis con excepción de Guatemala de donde solo un ejemplar fué disponible y dos para L. gomezi.
El fragmento de 380 pb fué amplificado usando los oligonucleótidos LRJ12966 (AAA AAA ATT ACG CTG TTA TCC CTA A) y LRN13393 (C (G/A)C CTG TTT AAC AAA AAC AT) diseñados y construídos en el Center for Diseases Control (Atlanta, Georgia) con base en la secuencia consensus de dos regiones altamente conservadas del gen de la unidad larga ribosomal mitocondrial de seis especies de invertebrados depositados en el banco de genes (Gen Bank). Las especies elegidas para diseñar los primers y los números de identificación en el banco de genes son las siguientes: Anopheles gambiae (L20934), Anopheles quadrimaculatus (LO4272), Apis mellifera (LO6178), Drosophila melanogaster (U37541) y Locustus migratoria (X80245).
Después de una fase inicial de desnaturalización del ADN a 94° C, durante tres minutos, los parámetros de amplificación para los siguientes 35 ciclos de PCR fueron: desnaturalización por un minuto a 93° C, alineamiento por un minuto a 50° C y extensión por 1 minuto a 72° C. Para verificar la amplificación, parte de la muestra fué sometida a electroforesis en un gel de agarosa al 1% con bromuro de etidio.
El ADN amplificado fue purificado usando Wizard PCR preps (Promega) para productos de PCR. Los productos de PCR fueron secuenciados directamente en ambos sentidos de la doble cadena usando un secuenciador automático ABI 377 (Perkin Elmer) y analizadas con el paquete GCG (Genetics Computer Group). Las secuencias fueron editadas usando el programa Sequencing Navigator (Perkin Elmer) comparando las secuencias en ambos sentidos de la doble cadena para cada especímen y posteriormente alineadas por el programa pileUp de GCG. La variabilidad haplotípica, la composición en términos de nucleótidos y el porcentaje de transiciones-transversiones entre las secuencias fueron igualmente determinadas.
Resultados
Amplificación de ADN mediante PCR.
La Figura 1 muestra la amplificación exitosa del fragmento de 380 pb de algunos de los especímenes visualizada en un gel de agarosa al 1%; el tamaño de la banda fué determina do por comparación con el marcador de peso molecular de 1 Kb (Promega) que aparece en las líneas extremas de la fotografía del gel. La identidad del fragmento fué corroborada posteriormente al comparar las secuencias con la secuencia referencia de Auoplieles gambiae (Beard
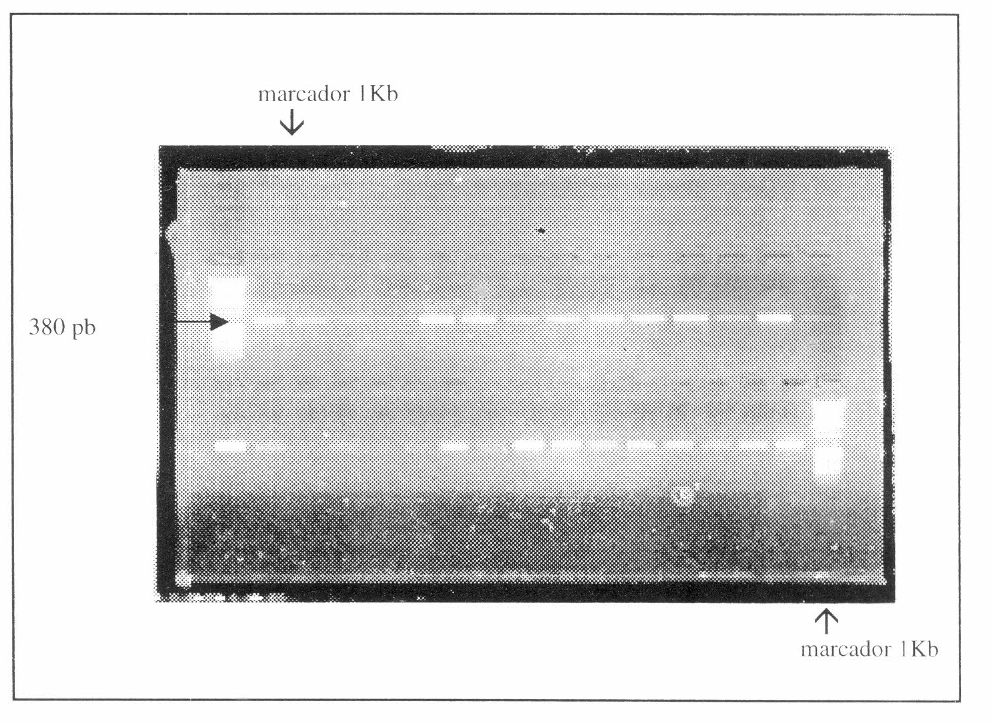
Verficación de la amplificación de mt lrRNA en gel de agarosa 1%. Los carriles de los extremos corresponden al marcador de peso molecular 1Kb (promega) Los otros carriles corresponden a productos amplificados por PCR y/o purificación (línea infe rior) en L. longipalpis de diferentes localidades y L. gomezi. C1: L. longipalpis El Callejón (Cundinamarca), C2: El Callejón especímen 2, C3: El Callejón especímen 3, C4: Girón (Santander), C5: Girón (Santander) especímen 2, C6:Girón (Santander) especímen 3, C7: Minas gerais (Brazil), C8: Minas gerais (Brazil), especímen 2, C9: Minas gerais (Brazil), especímen 3, C10: Sobral ceará (Brazil) C11: Sobral ceará (Brazil), especímen 2, C12: Sobral ceará (Brazil), especímen 3, C13: Tulumajillo (El Progreso, Guatemala) C14: Trujillo (Venezuela), C15: Trujillo (Venezuela), especímen 2, C16: Trujillo (Venezuela), especímen 3, C18: L. gomezi (Montebello), C20: L. gomezi (Montebello) especímen 2. Los carriles C21-C230 corresponden a los productos de PCR purificados de los productos de PCR visualizados en los carriles C1-C10.
Secuencias.
Las secuencias obtenidas para LU1ZOl11yia corresponden a las posiciones 12904 - 13284 de la secuencia referencia de Anopheles gambiae y la homología entre ellas fué de 80 % para L. gomezi y 79.8 % para L. langipalpis.
La composición de las bases fué similar en todas las secuencias de Lutromvia. las cuales aparecen en la Figura 2. las proporciones de las bases variaron entre 36.8-41 % para timina, 38.6-41.5 para adenina, 5.5-8.8 para guanina y 9.4-10.8 para citosina.
Los porcentajes promedio de cada una de las bases fueron:
A: 42%. T: 39o/c. O: 8%, y C: II %. Altas proporciones de adenina-tirnina (81 %) en total son consistentes con la composición de estos nucleótidos encontrada en secuencias de ADN mitocondrial en otros insectos (Simond
En el alineamiento múltiple de pileUp bajo OCO (Fig. 3) se observaron 14 haplotipos entre las 18 secuencias. Un haplotipo es definido en la vía usual. es decir, como una secuencia única de ADN rnitocondrial que puede dis mguirse de cualquier otra secuencia homóloga por lo menos por una substitución nucleotídica. Los haplotipos comunes en dos o más individuos fueron encontrados solo en
Al comparar las secuencias entre
Variaciones puntuales como éstas son frecuentemente observadas entre insectos de la misma especie. en particular cuando los especímenes estudiados provienen del campo (Besanski
Algunas diferencias encontradas entre
El hecho de que el alineamiento de las secuencias obtenidas directamente deproductos de PCR no revelara arnbiguedades características de heteroplasmia dentro o entre las dos especies. sugiere que los segmentos secuenciados corresponden a ADN mitocondrial y no a copias nucleares (Besan ski el 01. 1997).
La comparación con secuencias homólogas previamente estudiadas en otros insectos y en especial con
Discusión
En este estudio se presentan las secuencias de un fragmento de 380 pb de la unidad larga ribosornal mitocondrial en
Numerosos estudios han mostrado que el ADN mitocondrial de insectos posee una proporción alta en adenina y timina y las
Por ejemplo, la región homóloga en 32 especies de cucarachas mostró' un promedio de 72% en A- T (Kambhapati 1995) y para miembros de la familia Cicadelidae. Fang
En el caso de
Igualmente, estudios similares en fragmentos más largos de la unidad larga ribosomal mitocondrial en insectos de la familia, Aphidiidae (Hymenoptera), y Lachnidae (l lornoptera). revelaron un contenido de A-T de aproximadamente 75% (Kambhampti datos no publicados).
En cuanto a las sustituciones nucleotídicas. el promedio de la tasa de transiciciones de 30%(entre
La tasa de transversiones de 70% fue más alta que la encontrada en otro, insectos. sin embargo. el porcentaje en las transversionesA-T fue menor respecto al de cucarachas) similar al de termitas (Kambhapati 1995: Kambhapati (
La variabilidad en las sustituciones nucleotídicas confirma la existencia de diferencias en la dinámica evolutiva del gen 16S rRNA entre grupos de insectos propuesta por Kambhampati
La variación en el contenido de A-T en secuencias de AD mitocondrial en insectos ha sido previamente demostrada y ha sido particularmente estudiada en Hymenoptera. donde la cantidad de A-T alcanza extremas proporciones (Crozier y Cro z ier 1989: Dietrich el (/1. 1997)
Investigaciones previas sugieren que las fluctuaciones en la composición de nucleótidos son consecuencia directa del tipo de evolución de DNA mitncondrial en insectos y que los efectos potencialmente adversos de esta variación en la taxonomía y reconstrucción filogenética deben ser considerados. por lo tanto. estudios haxado» en secuencias como las de Hyrnenoptera y
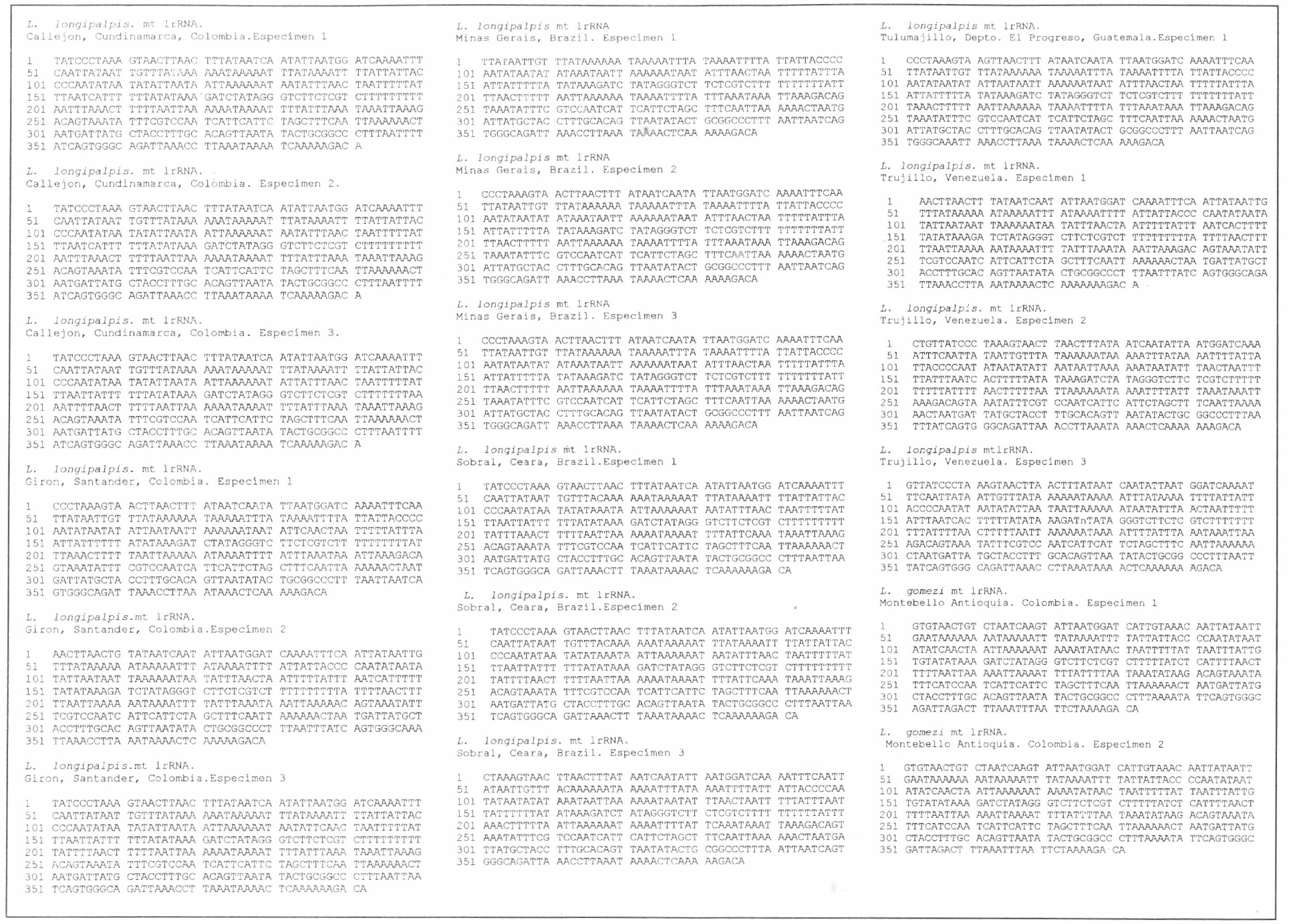
Secuencias del fragmento de la unidad larga ribosomal obtenidas a partir de especímenes de
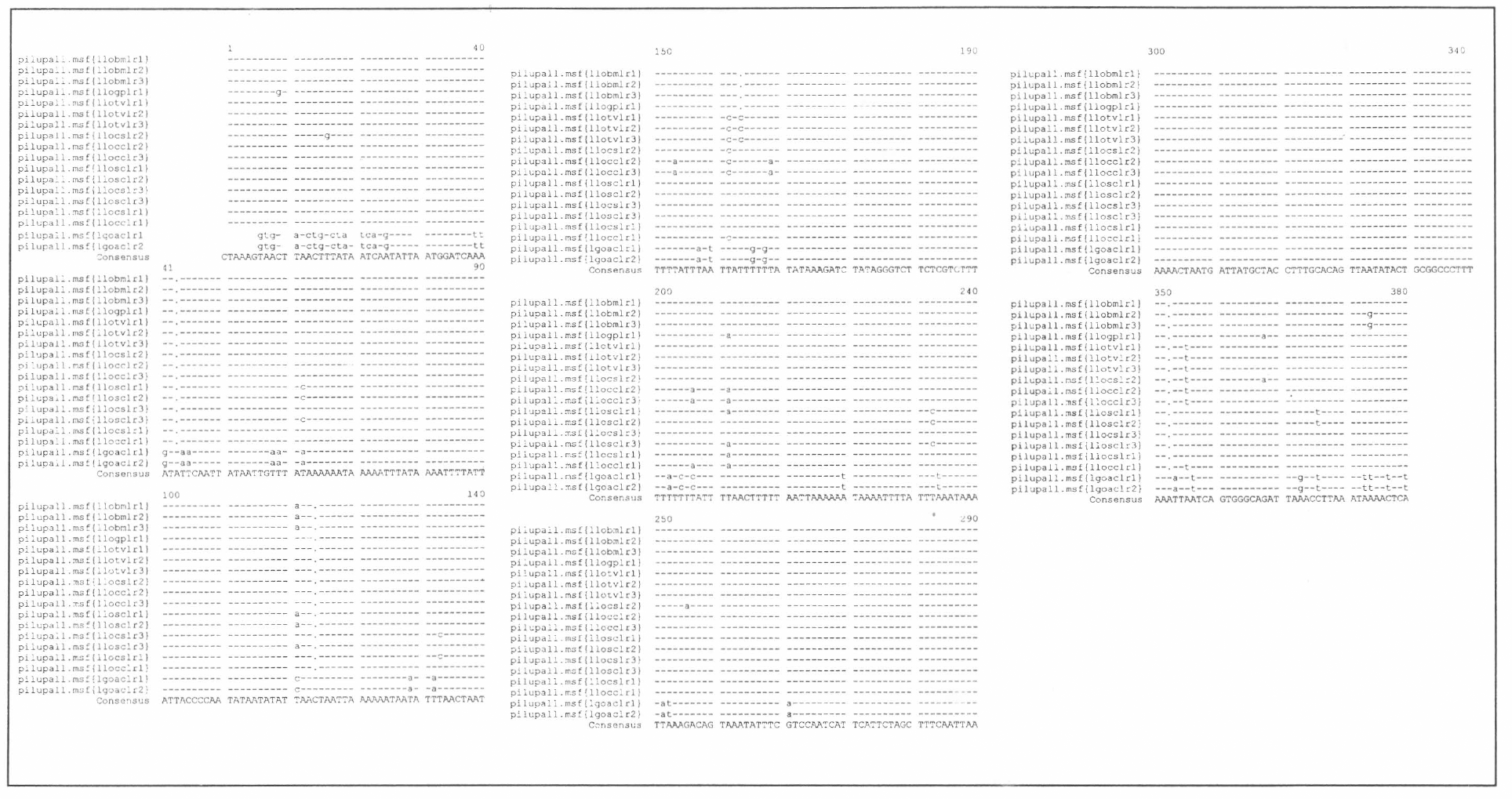
Alineamiento múltiple de las secuencias de mt IrRNA bajo PileUp programa GCG (Genetic Computer Group) para
La gran cantidad de A-T presente en ADN mitocondrial de insectos ha sido explicada asumiendo que por razones desconocidas existe un fenómeno evolutivo que hace que las enzimas involucradas en la transcripción y replicación de ADN rico en A-T han evolucionado para hacer este proceso más efectivo que en el caso de G-C; (Wolstenholme y Clary 1985; Crozier
El número de diferencias en términos de nucleótidos a nivel de especie entre
Finalmente, es importante considerar que a pesar del desarrollo reciente de la metodología molecular para el estudio de insectos, la identificación y el aislamiento de secuencias útiles a determinados niveles de divergencia, continúa siendo problemático (Doolittle
Conclusiones
Los oligonucleótidos LRJ 2966 y LRN 13393, diseñados con base en las secuencias de insectos como
Las secuencias de la unidad larga ribosomal obtenidas de Lutzomyia poseen una alta proporción de A-T (81%) y un porcentaje de transiciones-transversiones similares a los descritos para regiones homólogas en otros insectos.
La amplificación y obtención de las secuencias de la unidad larga ribosomal mitocondrial a partir de
El polimorfismo de las secuencias en términos de nucleótidos a nivel intra e inter específico, observado en los alineamientos múltiples, sugiere la utilidad de este fragmento como criterio taxonómico a nivel de especie para especies del género
La estandarización de técnicas de PCR y la obtención de secuencias de ADN a partir de insectos de importancia agrícola o médica como
Footnotes
Agradecimientos
Los autores desean agradecer a COLCIENCIAS y la Universidad de Antioquia CODI por la beca y coofinanciación que permitieron el desplazamiento de Sandra Uribe al Center for Diseases Control en Atlanta Georgia y la realización exitosa de este trabajo.
