Abstract
Bacillus thuringiensis (Bt) subsp. medellin (Btmed) produces parasporal crystalline inclusions which are toxic to mosquito larvae. It has been shown that the inclusions of this bacterium contain mainly proteins of 94, 68 and 28-30 kDa. EcoRI partially digested total DNA of Btmed was cloned by using the Lambda Zap II cloning kit. Recombinant plaques were screened with a mouse policlonal antibody raised against the 94 kDa crystal protein of Btmed. One of the positive plaques was selected, and by in vivo excision, a recombinant pBluescript SK(-) was obtained. The gene encoding the 94 kDa toxin of Btmed DNA was cloned in a 4.4 kb DNA fragment. Btmed DNA was then subcloned as a EcoRI/EcoRI fragment into the shuttle vector pBU4 producing the recombinant plasmid pBTM3 and used to transform by electroporation Bt subsp. israelensis (Bti) crystal negative strain 4Q2-81. Toxicity to mosquito larvae was estimated by using first instar laboratory reared Aedes aegypti, and Culex quinquefasciatus larvae challenged with whole crystals. Toxicity results indicate that the purified inclusions from the recombinant Bti strain were toxic to all mosquito species tested, although the toxicity was not as high as the one produced by the crystal of the Btmed wild type strain. Poliacrylamide gel electrophoresis indicate that the inclusions produced by the recombinant strain Bti (pBTM3) were mainly composed of the 94 kDa protein of Btmed, as it was determined by Western blot.
Introducción
Durante los últimos años los programas de control de mosquitos a nivel mundial han estado evaluando la posibilidad de implementar estrategias de control biológico utilizando Bacillus thuringiensis (Bt) subsp. israelensis (Bti) ó B. sphaericus (Bs). Bt es una bacteria entomopatógena que produce inclusiones cristalinas paraesporales tóxicas a larvas de insectos susceptibles cuando son ingeridas y es un candidato promisorio para reemplazar los insecticidas químicos nocivos (Porter et al. 1993). Las cepas más tóxicas de Bt para el control de mosquitos son aquellas señaladas por Goldberg y Margalit (1977), Padua et al. (1984), Orduz et al. (1992, 1994), Seleena et al. (1995) y Ragni et al. (1996).
Las inclusiones cristalinas paraesporales de Bti contienen cuatro polipéptidos mayores con masas moleculares de 135, 125, 68 y 28 kDa, las cuales son referidas como CryIVB, CryIVA, CryIVD y CytA, respectivamente, de acuerdo con la clasificación designada por Höfte y Whiteley (1989) y pertenecientes a los grupos Cry4A, Cry4B, Cry11A y Cyt1A de la clasificación propuesta por Dean (comunicación personal). Análisis de las inclusiones cristalinas paraesporales purificadas de Btmed сера СІВ 163-131 mediante electroforesis en gel de sodio dodecil sulfato-poliacrylamida (SDS-PAGE) muestran polipéptidos de aproximadamente 94 kDa, múltiples bandas de 80, 75, 70, 67, 65 kDa y dos dobletas de 40-41 y 28-30 kDa y la matriz de las inclusiones paraesporales cristalinas de Btmed determinada por microscopía electrónica es similar a la observada en Bti (Orduz et al. 1994).
Los genes que codifican los cuatro polipéptidos del cristal de Bti han sido clonados y el análisis de los productos de los genes clonados ha esclarecido resultados preliminares controversiales sobre la interacción de las diferentes proteínas del cristal y su resultante toxicidad hacia larvas de mosquito (Angsuthanasombat et al. 1992; Delécluse et al. 1993; Poncet et al. 1993, 1995; Wu et al. 1994). Recientemente, el gen que codifica la proteína tóxica de 80 kDa de Bt subsp. jegathesan (Btj) ha sido clonado y sequenciado. Se encontró que el producto del gen posee un 58% de homología con Cry11A y, por lo tanto, fue denominado Cry11B y la toxicidad del producto recombinante fue mayor para larvas de Aedes aegypti que la cepa nativa (Delécluse et al. 1995). El papel de la proteína de 94 kDa de Btmed en la toxicidad aún no es claro, aunque Orduz et al. (1996), después de la purificación de las toxinas de Btmed por cromatografia en una columna de exclusión, han sugerido que la proteína de 94 kDa es, probablemente, el componente más importante de la inclusión cristalina paraesporal en la toxicidad hacia larvas de Culex quinquefasciatus.
En este artículo se registra primero, el clonaje de un fragmento de ADN que codifica la proteína de 94 kDa del cristal de Btmed en una cepa cristal negativa de Bti y su expresión y, segundo, la toxicidad de inclusiones purificadas producidas por la cepa de Bti recombinante comparada con la toxicidad producida por cristales purificados de las cepas nativas CIB 163-131 de Btmed y 1884 de Bti contra larvas de primer estadio de A. aegypti y C. quinquefasciatus.
Materiales y Métodos
Cepas bacterianas
Bti 4Q2-81, una cepa cristal negativa curada de todos los plásmidos residentes, fue utilizada como receptora para los experimentos de transformación la cual fue atentamente suministrada por D. Dean (The Ohio State University, USA). La cepa 1884 de Bti, aislada de Israel, es preservada en el International Entomopathogenic Bacillus Centre del Institut Pasteur Culture Collection. La сера СІВ 163-131 de Btmed fue aislada en Colombia (Orduz et al. 1992). Estas bacterias formadoras de esporas son preservadas como esporas, en papel de filtro estéril empacado en ampollas selladas, en la Colección de Bacterias de la Corporación para Investigaciones Biológicas. Las cepas XL1-Blue MRF' y SOLR de Escherichia coli, utilizadas para las manipulaciones genéticas, fueron obtenidas de Stratagene (La Jolla, CA, USA).
Clonaje del gen
Una librería genómica de Btmed cepa CIB 163-131 fue generada usando el kit de clonaje Lambda Zap II/EcoRI/ CIAP (Stratagene, La Jolla, CA, USA). El ADN total de Btmed se aisló, parcialmente digerido con EcoRI y ligado al vector como recomienda el fabricante. El ADN Lambda Zap se empacó in vitro y se utilizó para infectar E. coli XL1-BLUE hospederas. La librería fue plateada y las placas fueron transferidas a membranas de nitrocelulosa para ser probadas con un antisuero producido en ratón contra la proteína de 94 kDa del cristal de Btmed (Orduz et al. 1996). Después de la purificación de las placas positivas, una de ellas fue seleccionada para su posterior caracterización. Un pBluescript SK(-) recombinante fue obtenido del vector Lambda Zap II por excisión in vivo y fue utilizado para la transformación de E. coli SOLR. El ADN plasmídico fue aislado de E. coli SOLR recombinantes y el mapa de restricción parcial del fragmento de ADN de Btmed fue determinado utilizando enzimas de restricción obtenidas de New England Biolabs (Beverly, MA, USA). El fragmento de ADN EcoRI/EcoRI de Btmed de este clon fue subclonado en el vector bifuncional pBU4 (Bourgouin et al. 1990) para producir el plásmido recombinante pBTM3 que fue utilizado para transformar por electroporación la cepa cristal negativa 4Q2-81 como describió Bone y Ellar (1989). Este vector de clonaje contiene un gen de resistencia a tetraciclina y la concentración utilizada para la selección de bacterias recombinantes fue de 30 ug/ml.
Purificación y solubilización de cristales
Cultivos de Btmed CIB 163-131, Bti y la cepa recombinante 4Q2-81 (pBTM3) de Bti fueron creciendo en tubos que contenían 5 ml de medio líquido UNO (por litro, Proflo 1 g, peptona 5 g, glucosa 3 g, KH₂PO₄ 6 g, solución de sales de cloruro 10 ml con 0.02 g de cada uno de los siguientes reactivos MgCl₂·6H₂O, MnCl₂·4H₂O, FeCl₂·6H₂O, ZnCl₂, y CaCl₂·2H₂O, buffer fosfato 200 ml, pH ajustado a 7.2, suplementado con tetraciclina (30 ug/ml) para 4Q2-81 (pBTM3). Los cultivos fueron incubados por 8 horas a 30°C у 200 rpm y, luego, transferidos a erlenmeyers con 50 ml medio líquido UNO y crecidos durante 12 horas. Finalmente, los cultivos fueron pasados a erlenmeyers que contenían 1 litro de medio líquido UNO e incubados durante 48 horas a 30°C y 200 rpm hasta su esporulación. Una vez confirmada la pureza de los cultivos por observación microscópica, las esporas, cristales y células lisadas fueron colectadas por centrifugación a 9,000 rpm, 4°C por 15 minutos y resuspendidas en 1/20 del volumen original en 1 M de NaCl y agitadas por 30 minutos a 37°C y 150 rpm para neutralizar la actividad de las proteasas. Después se lavaron dos veces con agua destilada y los botones resultantes fueron resuspendidos en 1/20 del volumen original en agua destilada, agitados con perlas de vidrio y sonicados tres veces por 15 segundos en un sonificador Branson.
Las inclusiones cristalinas paraesporales de Btmed, Bti y la cepa recombinante 4Q2-81 (pBTM3) de Bti fueron purificadas por el método descrito por Pendleton y Morrison (1966). Este método utiliza CCl₄, 1% de Na₂SO₄ y agua destilada estéril y separa los cristales en un embudo de separación. Los cristales purificados se lavaron tres veces con agua destilada estéril y se concentraron por centrifugación durante 10 minutos a 4º C y 10,000 rpm. Finalmente, los cristales fueron resuspendidos en 5 ml de agua estéril, aliquotados, liofilizados y almacenados a 4°C hasta su uso. Quince miligramos de cristales de cada cepa se suspendieron en 1 ml de agua destilada estéril. Quinientos microlitros (ul) de esta suspensión se mezclaron con 2 ml de un buffer, pH 11.3 y se agitaron lentamente por 24 horas a 30°C y 250 rpm como describió Koller et al. (1992). Las proteínas solubilizadas se dializaron contra un buffer salino fosfato (PBS), pH 7.2 (por litro: Na₂HPO₄ 1.44 g, NaCl 8 g, KCl 0.2 gr, KH₂PO₄ 0.24 g). Después de la solubilización, la concentración de proteínas fue medida por la técnica de BioRad (Hercules, CA, USA), utilizando el protocolo de microensayo. Una curva estandar fue construida con gamma globulina bovina.
Actividad tóxica de cristales purificados de cepas de Bacillus thuringiensis en larvas de primer estadío de dos especies de mosquito.
: el valor representa el promedio de tres ensayos. Los números en paréntesis corresponden a los límites de confianza (95%) determinado por análisis Probit. Btmed, Bacillus thuringiensis subsp. medellin; 4Q2-81, cepa cristal negativa de Bti portando el fragmento de ADN que codifica el gen tóxico de la proteína de 94 kDa; Bti, Bacillus thuringiensis subsp. israelensis; 4Q2-81, cepa cristal negativa de Bti; NT no tóxica.
Electroforesis y Western blot
Para determinar la expresión de la proteína de 94 kDa de Btmed en la cepa recombinante 4Q2-81 (pBTM3) de Bti, las proteínas fueron separadas por electroforesis en un gel de sodio dodecil sulfato-poliacrylamida (SDS-PAGE 10%, acrylamide-bis-N-N' acrylamide). Después de la separación, las proteínas fueron electro-transferidas a membranas de nitrocelulosa e incubadas para la detección inmunológica con el anticuerpo anti-94 kDa (Orduz et al. 1996), seguido por incubación con proteína A conjugada a fosfatasa alcalina. Después de esta incubación, fue adicionado un sistema de sustrato/color compuesto de naftol fosfato/fast red (Sigma Chemical Co.).
Ensayos de toxicidad
Las larvas de A. aegypti y C. quinquefasciatus utilizadas en este experimento, fueron colectadas en cercanías de Medellín. Las especies de mosquitos se mantuvieron bajo condiciones de laboratorio a 30±2°C bajo un fotoperíodo 12:12 (luz:oscuridad). Los bioensayos fueron realizados utilizando preparaciones de inclusiones paraesporales liofilizadas de cada una de las cepas de Bt. Quince miligramos de preparación de inclusiones paraesporales liofilizadas fueron suspendidas en 1 ml de agua destilada estéril y seriadamente diluido en 0.9 ml de agua destilada estéril. Diferentes cantidades de estas diluciones fueron probadas contra larvas de A. aegypti y C. quinquefasciatus. Se colocaron cinco larvas de primer estadío en cada uno de los veinticuatro pozos de un microplato con 1 mililitro de agua desionizada, la suspensión fue adicionada de inclusiones paraesporales y finalmente, de 5 miligramos de soya trucha. Tres replicas, consistentes de tres pozos por dilución fueron incluidos y ensayados en tres días diferentes. Luego de veinticuatro horas se determinó la mortalidad larval. La concentración letal media (LC₅₀) fue calculada por análisis Probit con la ayuda de un programa de computador diseñado por E. Franhon (Institut Pasteur, París).
Resultados
Caracterización y análisis del clon 3A6-1A
El análisis de la librería genómica de Btmed permitió obtener placas recombinantes expresando la proteína de 94 kDa de la cepa CIB 163-131 de Btmed ya que fue reconocida por el correspondiente antisuero de ratón. De una de las placas positivas seleccionadas (3A6-1A), el plásmido recombinante pBluescript fue obtenido por excisión in vivo. Este plásmido contiene un inserto EcoRI de 4.4 kb portando el gen de la proteína de 94 kDa. El mapa de restricción parcial del fragmento de ADN de 4.4 kb de Btmed se muestra en la figura 1. Este fragmento fue luego subclonado en el vector bifuncional pBU4, el cual es capaz de replicarse en Bt y luego introducido por electroporación en la cepa cristal negativa 4Q2-81 produciendo la сера 4Q2-81 (pBTM3).
Expresión de la proteína de 94 kDa de Btmed en la cepa cristal-negativa 4Q2-81
Observaciones microscópicas de un cultivo de 48 horas de la células recombinantes conteniendo el fragmento de ADN que codifica la proteína de 94 kDa del cristal de Btmed reveló la presencia de grandes inclusiones paraesporales las cuales en general fueron más grandes que aquellas producidas por las cepas nativas CIB 163-131 de Btmed y 1884 de Bti. Inclusiones purificadas y liofilizadas de las cepas de Bt fueron sujetas a SDS-PAGE y el gel fue coloreado con Azul de Coomasie brillante (Fig 2A). El cristal de la cepa nativa CIB 163-131 de Btmed presentó cuatro polipéptidos mayores de 94, 68 y 28-30 kDa (Fig 2A, línea 1). La preparación enriquecida de inclusiones cristalinas paraesporales de la cepa recombinante 4Q2-81 (pBTM3) presentó un polipéptido mayor de 94 kDa el cual tiene la misma movilidad electroforética que el polipéptido más grande en el cristal de la cepa nativa CIB 163-131 (Fig 2A, línea 2). En el Western blot, la proteína recombinante sintetizada por la сера 4Q2-81 (pBTM3) de Bti comigró con la proteína de 94 kDa del cristal de Btmed en SDS-PAGE y éste fue el único polipéptido reconocido por el anticuerpo anti-94 kDa (Fig. 2B, línea 2) y ninguna proteína fue reconocida por el antisuero de ratón en la inclusión cristalina paraesporal de Bti (Fig. 2B, línea 3).
Toxicidad de la proteína de 94 kDa
El fragmento de ADN que codifica la proteína de 94 kDa del cristal de Btmed clonado y expresado en E. coli SOLR produjo significativa mortalidad cuando se suministraron células completas a larvas de tercer estadío de C. quinquefasciatus con y sin inducción por 24 horas con isopropiltio-8-D-galactoside (dato no mostrado). Inclusiones purificadas y liofilizadas de la cepa CIB 163-131 de Btmed, cepa 1884 de Bti, cepa 4Q2-81 (pBTM3) de Bti y cultivo completo final de la cepa 4Q2-81 de Bti se ensayaron para actividad tóxica con larvas de primer estadío de A. aegypti y C. quinquefasciatus. Las inclusiones producidas por la cepa recombinante 4Q2-81 (pBTM3) de Bti, que expresan el polipéptido de 94 kDa de Btmed, y las cepas nativas CIB 163-131 de Btmed y 1884 de Bti fueron tóxicas a las especies de mosquito probadas (Tabla 1). Aunque una susceptibilidad diferencial por especie de mosquito a la misma proteína tóxica de 94 kDa de Btmed fue observada en todas las especies, las inclusiones recombinantes no fueron tan activas como los cristales producidos por las cepas de Btmed y Bti y tuvo una LC₅₀ de 43 ng/ml, la cual es aproximadamente 4 veces más baja que la toxicidad producida por la cepa nativa de Btmed en larvas de C. quinquefasciatus y 69.6 ng/ml la cual es 9 veces más baja en larvas de A. aegypti. La toxicidad de la cepa nativa 1884 de Bti fue 17 veces más alta que la cepa recombinante 4Q2-81 (pBTM3) de Bti en larvas de A. aegypti y aproximadamente 9 veces más alta en larvas de C. quinquefasciatus.
Discusión
Para esclarecer el papel del polipéptido de 94 kDa del cristal de Btmed en la toxicidad hacia larvas de mosquito, se realizaron experimentos de clonaje y bioensayos con las inclusiones purificadas producidas por una cepa recombinante de Bti portando el fragmento de ADN la cual codifica esta proteína. La cepa recombinante 4Q2-81 (pBTM3) de Bti expresó el gen de la proteína tóxica de 94 kDa de Btmed a niveles altos y las células huésped fueron capaces de empacar la proteína como una inclusión paraesporal visible bajo microscopio de luz. El tamaño de la inclusión paraesporal producida por la cepa recombinante 4Q2-81 (pBTM3) de Bti fue más grande que el producido por las cepas nativas de Btmed y Bti, contrario a los resultados de Delécluse et al. (1993) quienes observaron que la cepa recombinante 4Q2-81 de Bti transportando el producto del gen cry4B produjo inclusiones más pequeñas, mientras la cepa recombinante 4Q2-81 de Bti transportando el gen cry4A no produjo inclusiones paraesporales cuando fue clonado en un plásmido de bajo número de copias, pero éstas fueron observadas cuando fue clonado en un plásmido de alto número de copias, en este caso, los cultivos esporulados fueron tóxicos a larvas de mosquito. El tamaño y las propiedades antigénicas de la proteína codificada por este fragmento de ADN es aparentemente no común a otras cepas de Bt activas a mosquitos aisladas a la fecha. Cuando se probó en bioensayos, la cepa recombinante 4Q2-81 (pBTM3) fue tóxica a larvas de primer estadío de A. aegypti y C. quinquefasciatus, confirmando la identidad del clon como una proteína insecticida del cristal de Btmed. Resultados preliminares de la actividad de proteínas individuales purificadas por tamaño en una columna de exclusión cromatográfica sugieren que la proteína de 94 kDa es quizás el componente más importante de la toxina de Btmed con la LC₅₀ más baja de 82.6 ng de proteína/ml contra larvas de C. quinquefasciatus (Orduz et al. 1996), contrario a la observación de Chilcott y Ellar (1988) en Bti donde ellos encontraron que en esta subespecie de Bt el componente más tóxico del cristal fue la proteína de 68 kDa. Se ha sugerido que las proteínas de 68 y 30 kDa de Btmed tienen un papel menor en la toxicidad hacia larvas de C. quinquefasciatus (Orduz et al. 1996).
La toxicidad de la proteína recombinante Cry4A de Bti es entre 21 y 22 veces más baja que la proteína recombinante de 94 kDa de Btmed en larvas de Aedes y Culex, como indicó el dato de toxicidad señalado por Angsuthanasombat et al. (1992), aunque hubo diferencias en la edad de las larvas en los dos bioensayos comparados. En el caso de la proteína recombinante Cry4B de Bti, Angsuthanasombat et al. (1992) han señalado valores de LC₅₀ de 940 y 24.500 ng/ml para A. aegypti y C. quinquefasciatus respectivamente, los cuales son 13.5 y 569 veces más bajos que la LC₅₀ encontrada para la proteína de 94 kDa de Btmed en la misma especie de mosquito. Los datos de toxicidad indicados por Delécluse et al. (1993) y Poncet et al. (1995) en mosquitos del género Aedes, Anopheles y Culex, cuando utlizaron proteínas recombinantes Cry4, son comparables con los señalados por Angsuthanasombat et al. (1992) para las mismas proteínas de Bti y por lo tanto tienen toxicidad más baja que la proteína recombinante de 94 kDa de Btmed. La toxicidad similar encontrada entre la proteína de 94 kDa de Btmed y Cry11A como señalaron Wu et al. (1994) sobre la misma edad larval de A. aegypti, sugieren que la proteína de 94 kDa de Btmed podría estar más relacionada con Cry11A que con Cry4A ó Cry4B. La toxicidad similar de las proteínas recombinantes Cry11B de Btj y la proteína de 94 kDa de Btmed indica que estas dos proteínas de Bt podrían estar muy relacionadas. La homología entre la proteína del cristal Cry 11A de Bti y la proteína del cristal Cry11B de Btj es del 58% (Delécluse et al. 1995). La secuencia similar entre Cry11A y Cry 11B y la toxicidad similar entre las proteínas del cristal Cry11A y 94 kDa de Btmed podrían indicar que estas tres proteínas están, en algún grado, relacionadas.
Experimentos adicionales con otros genes cry de Btmed que codifican los polipéptidos de 68 y 30 kDa son necesarios para esclarecer el sinergismo entre los componentes del cristal y el modo de acción de la proteínas tóxicas de Btmed. El progreso en el análisis de la secuencia del fragmento de ADN de 4.4 kb que codifica la proteína tóxica de 94 kDa de Btmed podría confirmar la relación evolutiva con otras proteínas del cristal de Bt.
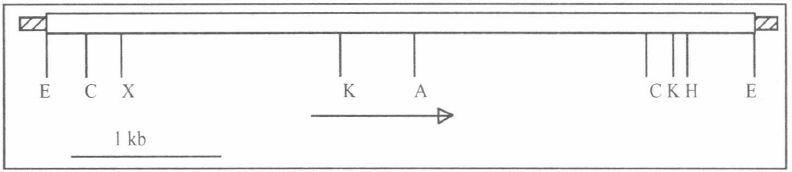
Mapa de restricción parcial del plásmido recombinante pBTM3 conteniendo el fragmento de ADN que codifica el gen tóxico de la proteína de 94 kDa de Bacillus thuringiensis subsp. medellin. La zona rayada corresponde al vector pBluescript. Abreviaturas: A, Acil; C, Clal; E, EcoRI; H, HindIII;, K, KpnI; X, Xbal. La flecha indica la dirección de transcripción.
Análisis de proteínas de las inclusiones de la cepa nativa de Bacillus thuringiensis subsp. medellin (Btmed), B. thuringiensis subsp israelensis (Bti) y la cepa recombinante 4Q2-81 (pBTM3). (A) 10 ug de inclusiones purificadas fueron sometidas a electroforesis sobre un gel al 10% de SDS-poliacrylamida. Línea 1, cepa nativa de Btmed CIB 163-131; línea 2, сера recombinante de Bti 4Q2-81 (pBTM3); línea 3, cepa 1884 de Bti. (B) Las inclusiones purificadas fueron sometidas a electroforesis como se mencionó y fueron transferidas a membrana de nitrocelulosa. La membrana fue probada con anticuerpos producidos contra la proteína tóxica de 94 kDa de Btmed. Para la inmunodetección fue utilizada proteína A conjugada a fosfatasa alcalina. Línea 1, cepa nativa de Btmed CIB 163-131; línea 2, cepa recombinante de Bti 4Q2-81 (pBTM3); línea 3, cepa 1884 de Bti.
Footnotes
Agradecimientos
Esta investigación recibió ayuda financiera de Colciencias, La Organización Mundial de la Salud (OMS), el Instituto Pasteur y la Corporación para Investigaciones Biológicas (CIB). Los autores agradecemos sus valiosas colaboraciones.
